UN ENFOQUE FILOGEOGRÁFICO PARA LA CONSERVACIÓN … Doctorado... · probablemente siendo una de...
-
Upload
truongdien -
Category
Documents
-
view
217 -
download
1
Transcript of UN ENFOQUE FILOGEOGRÁFICO PARA LA CONSERVACIÓN … Doctorado... · probablemente siendo una de...

UN ENFOQUE FILOGEOGRÁFICO PARA LA
CONSERVACIÓN DE POBLACIONES DE Ara macao
cyanoptera
TESIS QUE PRESENTA LUIS MANUEL GARCÍA FERIA
PARA OBTENER EL GRADO DE DOCTOR EN CIENCIAS
ECOLOGÍA Y MANEJO DE RECURSOS NATURALES
Xalapa, Veracruz, México 2009.

2
Aprobación final del documento final de tesis de grado:
Nombre Firma
Director Dr. Alejandro Espinosa de los Monteros ________________________
Comité Tutorial Dr. Jorge González Astorga ________________________
Dr. Daniel Piñero Dalmau ________________________
Dr. Adolfo Navarro Sigüenza ________________________
Jurado Dr. Octavio Rojas Soto ________________________
Dra. María del Coro Arizmendi ________________________
Dra. Carla Gutiérrez Rodríguez ________________________

3
DECLARACIÓN
Excepto cuando es explícitamente indicado en el texto, el trabajo de investigación
contenido en esta tesis fue efectuado por Luis Manuel García Feria como estudiante de la carrera
de Doctorado en Ciencias en Ecología y Manejo de Recursos Naturales entre agosto de 2004 y
marzo del 2009, bajo la supervisión del Dr. Alejandro Espinosa de los Monteros Solís.
Las investigaciones reportadas en esta tesis no han sido utilizadas anteriormente para
obtener otros grados académicos, ni serán utilizadas para tales fines en el futuro.
Candidato: _____________________________
Luis M. García Feria
Director de tesis: _____________________________
Dr. Alejandro Espinosa de los Monteros

7
ÍNDICE
RESUMEN ……………………………………………………………………………… 11
ABSTRACT ……………………………………………………………………………… 12
INTRODUCCIÓN ……………………………………………………………………… 13
CAPÍTULO I.
VARIACIÓN GENÉTICA COMO UNA GUÍA DE CONSERVACIÓN PARA
POBLACIONES CAUTIVAS Y SILVESTRES DE LA GUACAMAYA ROJA
(Ara macao cyanoptera) ………………………………………………………………… 19
Resumen ………………………………………………………………………… 21
Abstract …………………………………………………………………………… 22
Introducción ……………………………………………………………………… 23
Materiales y métodos …………………………………………………………… 24
Resultados ……………………………………………………………………… 26
Discusión ……………………………………………………………………… 27
Conclusión ……………………………………………………………………… 28
Agradecimientos ………………………………………………………………… 29
Literatura citada ………………………………………………………………… 29
CAPÍTULO II.
THE EFFECT OF THE MAYAN FOREST FRAGMENTATION ON THE
GENETIC STRUCTURE OF THE MESOAMERICAN SCARLET MACAW
(Ara macao cyanoptera) ………………………………………………………………… 39
Abstract ………………………………………………………………………… 41
1. Introduction ……………………………………………………….………… 42
2. Materials and Methods ……………………………………………………… 43
2.1 DNA Samples ……………………………………………………… 44

8
2.2 Genetic analyses ………………………………………………… 45
3. Results ………………………………………………………………………… 46
3.1. DNA polymorphism ………………………………………………… 46
3.2. Genealogical and population inferences …………………………… 47
4. Discussion and conclusions …………………………………………………… 49
4.1. Recent population history …………………………………………… 49
4.2. Mayan Forest fragmentation ………………………………………… 50
Acknowledgements ……………………………………………………………… 52
References ……………………………………………………………………… 53
CAPÍTULO III.
DISCUSIÓN GENERAL ………………..……………………………………………… 69
Implicaciones de manejo ………………………………………………………… 75
CONCLUSIÓN GENERAL …………………………………………………………… 77
REFERENCIAS ………………………………………………………………………… 79

9
LISTA DE FIGURAS
Figura 1. Distribución histórica y actual de Ara macao cyanoptera ……………… 14
CAPÍTULO I.
Figura I.1. Frecuencias y distribución de haplotipos en las cuatro poblaciones
geográficas muestreadas para Ara macao cyanoptera …………………………… 34
Figura I.2. Distribución y red de haplotipos para el gen mitocondrial de ND2 … 35
Figura I.3. Árbol más parsimonioso que muestra las interrelaciones históricas
entre los 51 individuos secuenciados para el gen mitocondrial ND2 …………… 36
CAPÍTULO II.
Figure II.1. Mesoamerican Scarlet macaw collection sites ……………………… 64
Figure II.2. Haplotype genealogy recovered after the Bayesian analysis ……… 65
Figure II.3. Minimum-length network for the 26 haplotypes of the Mesoamerican
Scarlet Macaw …………………………………………………………………… 66
Figure II.4. Mismatch distribution plots ………………………………………… 67

10
LISTA DE CUADROS Y TABLAS
CAPÍTULO I.
Cuadro I.1. Listado de haplotipos y sitios segregados ……………………………… 32
Cuadro I.2. Descriptores de la variabilidad genética para las cuatro
poblaciones geográficas de Ara macao cyanoptera ………………………………… 32
Cuadro I.3. Índice de fijación genética GST entre cuatro poblaciones de
Ara macao cyanoptera ……………………………………………………………… 33
CAPÍTULO II.
Table II.1 - Haplotype list and distribution ………………………………………… 61
Table II.2 - Genetic diversity and demographic parameters within the Scarlet
Macaw populations ………………………………………………………………… 62
Table II.3 - Fixation index and genetic structure by Analysis of Molecular
Variance of Scarlet macaw populations …………………………………………… 63
Table II.4 – Population pairwise values. Absolute number of migrants per
generation (M) above the diagonal, and fixation index (Fst) below the diagonal … 63
CAPÍTULO III.
Cuadro III.1. Superficie estimada de sitios de presencia de Ara macao cyanoptera
y correlación entre el tamaño del área de distribución (log) y descriptores de
variabilidad genética en las poblaciones de Ara macao cyanoptera ……………… 74

11
RESUMEN
Gran número de especies de aves se encuentran en peligro de extinción. Uno de los grupos en
mayor peligro son los psitácidos y entre ellos, la subespecie Mesoamericana de la guacamaya roja
(Ara macao cyanoptera). Su número estimado es de menos de 1 000 individuos distribuidos en
poblaciones pequeñas y aisladas en las selvas alta perennifolia y mediana subcaducifolia de
México y Centro América. Las principales causas del declive poblacional son la pérdida y
fragmentación del hábitat, el tráfico ilegal, los asentamientos humanos, desplazamiento de los
sitios de nidación con las abejas africanizadas y el aislamiento poblacional. Estas causas, a su
vez, son factores que influencian la pérdida de diversidad genética. Los objetivos principales
fueron la identificación de marcadores moleculares en las poblaciones silvestres de A. m.
cyanoptera, evaluación de la estructura genética, identificación de la distribución de la variación
genética y propuestas de manejo y conservación in situ y ex situ. Los datos obtenidos nos
revelaron la existencia de haplotipos endémicos a las poblaciones muestreadas y una diversidad
haplotípica mayor a la esperada, resultando en una relativa alta diversidad genética dentro de las
poblaciones. Sin embargo, la diversidad nucleotídica fue baja en comparación a otras especies en
peligro de extinción. A pesar de que existe asimetría en el flujo genético entre las poblaciones,
probablemente siendo una de las causas la reciente fragmentación de la Selva Maya, existe poca
diferenciación entre estas constituyendo una unidad reproductiva cohesiva. Los niveles de
variación entre poblaciones sugieren diferentes historias entre el crecimiento y la estabilidad
poblacional recientes. No obstante, se estima que el número efectivo de la población es
aproximadamente 113 individuos. Se conjetura que actualmente la pérdida del hábitat no ha
generado un efecto irreversible en la variabilidad genética de la especie; a pesar de que sí existe
una alarmante reducción en el número de individuos silvestres, con el consiguiente efecto en el
tamaño efectivo de la población, que podrían ocasionar a corto plazo la pérdida de haplotipos
locales y una probable subsecuente extinción. La estrategia sugerida con este trabajo es preservar
áreas grandes con poblaciones sustentables y promover el movimiento de individuos entre estas
áreas.

12
ABSTRACT
Many bird species are threatened by extinction. Psittacids is one of groups considered in high
risk. This is particularly the case of the Mesoamerican subspecies of the Scarlet macaw (Ara
macao cyanoptera). Specialists have estimated that in the wild only remain 1 000 individuals in
small populations scattered along the tropical forest of Mexico and Central America. The main
threats are habitat destruction, illegal trade, competence for nesting sites with African bees, and
urbanization. This population decline has resulted in a reduction in genetic diversity. The
objectives of my dissertation were: to identify potential molecular markers for the wild
populations of A. m. cyanoptera; to quantify the its genetic structure; to characterize this genetic
structure in space; and to suggest strategies for conservation in the wild and in captivity. The
results showed the existence of endemic haplotypes to the sampled populations. Albeit a low
nucleotide diversity, most parameters of genetic diversity were higher than expected. One of the
consequences of the recent fragmentation of the Mayan Forest is the disruption of the gene flow
among the macaw populations. Nonetheless, not enough time has passed to produce independent
genetic structure between them. The subspecies, therefore, remain as a cohesive reproductive
unit. Genetic descriptors suggest differences in the demographic history of those populations.
Whereas some of them are going through demographic stasis, others are growing. From the
genetic data, I was able to estimate an effective population size of 113 individuals. Apparently,
even though there is a rampant destruction in the Mayan Forest, the genetic variation within the
Mesoamerican scarlet macaw is in good condition. The number of wild individuals, nonetheless,
is declining rapidly. Therefore, if the threaten sources are not cease to happened, in the near
feature there would be a loss of haplotypes and finally the extinction of the subspecies.
Maintaining a Mesoamerican Biological Corridor is probably one of the best strategies for
increasing the survival probabilities of this bird.

13
INTRODUCCIÓN
En los últimos siglos las actividades del hombre han provocado severos impactos
negativos sobre el ambiente. Año con año, un número indeterminado de especies desaparece de
la faz de la Tierra, perdiéndose irrevocablemente parte de la herencia biológica (Erlich y Erlich
1981). El 11.5% de las especies de aves en el mundo, están amenazadas de extinción (Bennett y
Owens 1997, BirdLife International 2000). Cientos de estas especies pueden perderse si no se
toman acciones de conservación en forma inmediata, ya que la tasa de extinción mundial para las
aves se incrementó de una especie cada 83 años a una especie cada cuatro años durante los
últimos cuatro siglos (Sheppard 1995).
Uno de los grupos de aves en mayor peligro son los psitácidos, ya que se ha creado una
demanda doméstica importante desde siglos. Sumado a esto, la presión por cacería, la pérdida y
fragmentación del hábitat han sido factores importantes en la declinación de la supervivencia de
poblaciones de psitácidos (Snyder et al. 2000). Por ejemplo, sólo en México, se capturan entre
65,000 y 78,500 psitácidos al año. De estos, mueren el 75% y es recuperado por decomisos solo
el 2% de lo traficado ilegalmente (Cantú Guzmán et al. 2007). Los animales asegurados por las
instituciones de gobierno son resguardados en los Centros Integrales para la Conservación e
Investigación de la Vida Silvestre (CIVS). Posteriormente, el 17% de los animales son
destinados para investigación, para cría en cautiverio en las Unidades de Manejo de Fauna
Silvestre (UMAS), y para exhibición a zoológicos. Un 27% es liberado y en ocasiones el 45%
muere en los CIVS (Cantú Guzmán et al. 2007).
Algunas de las poblaciones silvestres de psitácidos han declinado entre 25 y 30% y si no
se detiene la captura ilegal, se prevé la eventual extinción de algunas especies. Se ha evaluado
que ni las vedas internacionales ni el mercado legal de mascotas están deteniendo el decline de
las poblaciones silvestres. Los psitácidos silvestres se siguen capturando y traficando ilegalmente
(Cantú Guzmán et al. 2007).
La guacamaya roja (Ara macao) es actualmente, una de las especies más amenazadas de
las 16 especies de guacamayas existentes en el Neotrópico. Esta ave está restringida a las selvas
ribereñas con vegetación de selva alta perennifolia y mediana subcaducifolia, desde el nivel del
mar hasta los 600 msnm (Wiedenfeld 1994). Se distribuía originalmente desde el noreste de

14
México hasta Brasil con una separación en su distribución entre Panamá y Sudamérica (Forshaw
y Cooper 1977; Juniper y Parr 1998).
La guacamaya roja había sido considerada por mucho tiempo una especie monotípica
(Forshaw 1977). Sin embargo, Wiedenfeld (1994) sugirió la existencia de dos subespecies: Ara
macao macao y A. m. cyanoptera. Históricamente, esta última subespecie se distribuía desde el
sur de Tamaulipas, hacia el sur en Veracruz, Oaxaca, Tabasco, Chiapas, Campeche, todo Belice,
a través del sur de Guatemala, Honduras, El Salvador, el centro de Nicaragua y una pequeña
porción al norte de Costa Rica (Wiedenfeld 1994, Juniper y Parr 1998). No obstante, en la
actualidad, la subespecie se ha reducido a tan solo un pequeño número de aves segregadas en
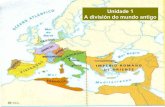
poblaciones aisladas (Wiedenfeld 1994; Fig. 1).
Figura 1. Distribución histórica y actual de Ara macao cyanoptera. El área sombreada
corresponde a la distribución histórica (InfoNatura 2007) y las áreas negras a reportes de las
poblaciones remanentes (CITES 2001).
Golfo de México
Mar Caribe
Océano Pacífico
800 Kilómetros0800

15
La guacamaya roja ha estado clasificada desde 1985 en el Apéndice I de la Convención
sobre el Comercio Internacional de Especies Amenazadas de Fauna y Flora Silvestres (CITES,
Sánchez et al. 1998). Inicialmente se incluyó en el Apéndice III en 1976, posteriormente, en el
Apéndice II en 1981 (UNEP-WCMC 2001). La tendencia por incrementar su protección se debió
al aumento del tráfico y comercio ilegales de individuos silvestres entre 1960 y 1985 (CITES
2001), sumado a la pérdida de hábitat y a la fragmentación de las poblaciones (Collar y Juniper
1992).
En el mismo contexto, esta especie no había sido considerada dentro de las categorías de
amenaza por Unión Internacional para la Conservación de la Naturaleza, UICN (Collar et al.
1992, Collar et al. 1994, Hilton-Taylor 2000). Recientemente se publicó el “Plan de Acciones de
Conservación y Muestreo de Psitácidos 2000-2004” (Snyder et al. 2000). En este Plan, Snyder et
al. (2000) señalan que el estatus de conservación de la especie debería ser cuidadosamente
revisado, particularmente la población de A. m. cyanoptera entre México y el norte de Costa
Rica, ya que debería ser incluida como un taxón en peligro. Debido a la extracción continua, las
poblaciones silvestres de guacamaya roja han declinado drásticamente en los últimos 20 años y
no se han podido recuperar, llegando a extinciones locales (Thurber et al. 1987, Iñigo-Elías y
Ramos 1991, Beissinguer y Bucher 1992, Iñigo-Elías 1996). Se estima que en México se
comercializan ilegalmente cerca de 50 guacamayas rojas al año (144 individuos en el periodo
1995-2005, Cantú et al. 2007).
Varias poblaciones de la subespecie Mesoamericana han sido extintas de la vertiente del
Pacífico en México, Guatemala, Honduras, Nicaragua (Wiedenfeld 1994) y El Salvador (Thurber
et al. 1987). Sin embargo, existen pequeñas poblaciones remanentes en la Selva Lacandona
(Forshaw 1989, Wiedenfeld 1994, Iñigo-Elías 1996), en Oaxaca (Binford 1989, Wiedenfeld
1994), en los bosques del suroeste de Belice (Kainer 1991, Manzanero 1991, Wiedenfeld 1994),
en el suroeste de la región del Petén en Guatemala (Wiedenfeld 1994, Pérez-Pérez 1998,
Carreón-Arroyo e Iñigo 1998), en el noreste de Honduras (Thorn 1991, Wiedenfeld 1994, Renton
2000) y el este de Nicaragua (Martínez-Sánchez 1991, Wiedenfeld 1994). Wiedenfeld (1994)
especula que podrían existir entre 3,000 y 4,000 ejemplares de A. m. cyanoptera entre México,
Guatemala, Belice, Honduras, Nicaragua y Costa Rica, en poblaciones altamente aisladas y
pequeñas. Por ello, su supervivencia a largo plazo parece ser poco probable.

16
En el 2001 se reunieron representantes de Belice, Guatemala y México con la finalidad de
definir un plan de acción y proteger a esta subespecie. En este momento, se estimaba que la
población de guacamayas rojas en la Selva Maya era de menos de 1000 individuos (Conservation
International 2001). La expansión de una agricultura y una ganadería poco productivas habían
transformado aceleradamente las selvas en paisajes empobrecidos donde la guacamaya roja no
podía sobrevivir (Conservation International 2001a). Además, debido a su alta fragmentación, el
número de individuos en algunas de las poblaciones silvestres era tan pequeño que muchas de
estas difícilmente podrían recuperarse, lo que podría llevarla a extinciones locales.
A pesar de la transformación que ha afectado a la Selva Maya, esta constituye la mayor
masa de bosque tropical en Mesoamérica. Es un mosaico de ecosistemas de gran importancia
para continuar la evolución y protección de las especies en vista de la constante reducción de la
cobertura boscosa y el cambio global (CIGyG 2005). Junto con la biodiversidad, el
mantenimiento de una alta variación genética dentro de las especies es de especial interés en la
Selva Maya (Conservation International 2004).
En muchas especies se ha observado un grado de estructuración genética diferente a los
individuos del centro de su distribución, llevando a los individuos del límite a mantener
características morfológicas y fenotípicas particulares (Herrera y Bazaga 2008). La variación
observada en estas poblaciones periféricas es de gran importancia para conservar el potencial
adaptativo de la especie (Antunes et al. 2006). Debido a que numerosas especies se encuentran en
el límite de sus áreas de distribución sur o norte, la extraordinaria diversidad biológica de la Selva
Maya contrasta con el hecho de que se trata de una región donde el deterioro ambiental es grave
(CIGyG 2005). Las causas de estas transformaciones son, principalmente, la conversión de los
bosques a áreas para ganadería y agricultura. Sin embargo, el crecimiento de los asentamientos
humanos es un factor de gran importancia, potencializado por la construcción de carreteras y
caminos creando así un fácil acceso para la extracción de recursos, entre ellos el petróleo, y la
madera (Hamann y Ankersen 1996, CIGyG 2005). En México, más del 60% de los 8,000 Km2 de
la Selva Lacandona ha sido deforestado desde 1970, perdiéndose 2,300 Km2 entre 1986 y 1996
(Hamann y Ankersen 1996).
La Reserva de la Biósfera Maya en Petén, Guatemala, cuenta con 1.3 millones de
hectáreas que representan la región más grande de área protegida. Sin embargo, la amenaza a la
cobertura vegetal es grande por la presión de las actividades humanas, yendo de una pérdida de

17
menos del 0.5% en los noventas, a una del 2% en la zona de amortiguamiento de la reserva en la
parte sur. Imágenes por satélite entre 1993 y 1995 demostraron una alta deforestación en el
Parque Nacional Laguna del Tigre (Guatemala) debido a la construcción de accesos para la
extracción de petróleo (Hamann y Ankersen 1996).
Como se comentó anteriormente, la fragmentación de las poblaciones silvestres puede
ocasionar extinciones locales que llegan a ser un problema muy grave y más cuando las
poblaciones son pequeñas y aisladas, lo cual disminuye el flujo genético entre ellas (Wright 1921,
Shonewald-Cox et al. 1983, Hedrick 2000). Malone et al. (2003) evaluaron el efecto de la
fragmentación poblacional en iguanas de la especie Cyclura cychlura, en las Bahamas. Debido a
los cambios climáticos del Pleistoceno, estas poblaciones muestran una alta diferenciación que no
está relacionada con la distancia geográfica. Además presentan una pérdida de diversidad
genética por deriva y endogamia, demostrando que las poblaciones grandes mantienen mayor
diversidad que las poblaciones pequeñas. Concluyendo así, que los eventos históricos tienen un
papel muy importante en los patrones de diversidad actuales. En otro estudio, Brown et al. (2004)
encontraron pérdida de diversidad nucleotídica en un corto periodo de tiempo debido al
aislamiento poblacional de aves neotropicales por el efecto de la fragmentación del hábitat. Un
caso mas es presentado por Barnett et al. (2008) quienes encuentran alta diferenciación entre las
poblaciones de Corapipo altera en bosques premontanos fragmentados de Costa Rica, sin
encontrar correlación entre los tamaños de los fragmentos y la diversidad genética.
Aparentemente, el hábitat fragmentado y el aislamiento entre las poblaciones de mono aullador
negro (Alouatta pigra) en la Selva Lacandona, México, son los responsables de una alta
diferenciación y variabilidad genética en esta especie (García del Valle et al. 2005). El estudio
del aislamiento y la subdivisión de las poblaciones también ha sido tema de investigación para la
conservación de diferentes especies y su hábitat. Ejemplos de ello son los quetzales,
Pharomachrus mocinno (Solórzano et al. 2004) y el mono aullador, Alouatta palliata (Milton et
al. 2008).
Basado en información sobre la problemática en la conservación de la Guacamaya roja
mesoamericana (Conservation International 2001a; Conservation International 2001b; CITES
2001; Cantú et al. 2007), así como en comentarios de expertos (Carreón e Iñigo-Elías 1998;
Takahashi 2006) respecto a la situación de esta especie, me he planteado los siguientes objetivos:

18
a) Identificar marcadores moleculares con niveles de variación que permitan el
reconocimiento de poblaciones silvestres de A. m. cyanoptera.
b) Evaluar la variación genética dentro y entre las poblaciones
c) Proponer estrategias de manejo tanto de las poblaciones cautivas como silvestres
de guacamaya roja mesoamericana.
Los resultados de la disertación son presentados en dos artículos a manera de capítulos. El
capítulo I muestra la estructura genética, y la distribución espacial de la variabilidad genética de
cuatro poblaciones geográficas de A. m. cyanoptera. Los análisis se basaron en un fragmento de
522 pb del gen mitocondrial ND2. Por lo tanto en este capítulo se presenta básicamente la
historia matrilineal. Dicho capitulo apareció publicado en el año de 2007 en el número 11 de la
revista Mesoamericana. En el capítulo II se presentan análisis equivalentes, para seis
poblaciones. En esta ocasión los resultados están basados en datos provenientes de dos
fragmentos mitocondriales (ND2 con 362 pb y ND5 con 337 pb) y un fragmento nuclear (RAG1
con 861 pb). Presentando, además de la descripción genética, la historia demográfica de cada
población. Este capítulo aun no ha sido publicado, pero se encuentra sometido para su
consideración en la revista Biological Conservation. Finalmente se presenta un cuarto capítulo
con conclusiones generales, así como recomendaciones de manejo de estas poblaciones,
individuos decomisados e individuos cautivos de origen silvestre.

19
CAPITULO I.
VARIACIÓN GENÉTICA COMO UNA GUÍA DE CONSERVACIÓN PARA POBLACIONES
CAUTIVAS Y SILVESTRES DE LA GUACAMAYA ROJA (Ara macao cyanoptera)
Luis Manuel García Feria
Alejandro Espinosa de los Monteros
Mesoamericana Volumen 11 Número 2 Año 2007.

20

21
Resumen
La destrucción del hábitat y el comercio ilegal de fauna silvestre es la causa principal de la
disminución en las poblaciones de psitácidos. La guacamaya roja de Centro América (Ara macao
cyanoptera) esta listada por la IUCN como especie en peligro. De la distribución histórica de esta
guacamaya solo quedan pequeñas poblaciones dispersas. El tamaño poblacional actual se estima
en 4000 individuos en pequeñas áreas aisladas en México, Belice, Guatemala, Honduras,
Nicaragua y Costa Rica. Las autoridades ambientales en Latinoamérica confiscan docenas de
estas aves cada año. No obstante, ya que se desconoce su origen muchas mueren en las áreas de
confinamiento. En el mejor escenario, los animales sobrevivientes son donados a zoológicos. El
objetivo del proyecto es identificar marcadores poblacionales por medio de secuencias de ADN
que sirvan para reconocer el origen geográfico de las guacamayas. Con ello, será posible tomar
medidas de reintroducción para las aves confiscadas. Complementariamente, los datos
recopilados de poblaciones silvestres nos dejarán deducir su estructura genética y el flujo
genético. Finalmente, la caracterización genética de los individuos cautivos permitirá establecer
un programa de reproducción que reduzca el riesgo por endogamia o la mezcla de linajes
genéticos incompatibles.
Palabras Claves: Ara macao cyanoptera, guacamaya roja, variación genética, conservación,
marcadores genéticos poblacionales.

22
Abstract
Habitat destruction and illegal wild-birds trade are the main reasons for psittacids’ population
decay. The Scarlet macaw from Middle America (Ara macao cyanoptera) is listed by the UICN
as an endangered species. Only scattered populations of this macaw remain from its original
historical distribution. Its population size has been estimated to 4000 individuals dispersed in
small isolated areas in México, Belize, Guatemala, Honduras, Nicaragua, and Costa Rica.
Environmental authorities in Latin America confiscate dozens of these birds every year.
Nonetheless, because their unknown origin most of them die in confinement areas. In the best
scenario, surviving animals are donated to zoos. This project’s goal is by means of DNA
sequences to identify wild population markers that will allow us to recognize the geographic
source of confiscated macaws. By pin pointing the origin of these birds reintroduction
measurements can be taken. The data gathered from wild populations will let us infer their
genetic structure and gene flow patterns. Finally, genetic surveys of captive individuals will
allow us to implement a breeding program that might reduce the inbreeding risk or incompatible
mix up of genetic lineages.
Key words: Ara macao cyanoptera, Scarlet Macaw, genetic variation, conservation, population
genetic markers.

23
Introducción
En los últimos siglos las actividades del hombre han provocado severos impactos negativos
sobre el ambiente (Erlich y Erlich 1981). En el mundo se estima que existen 9,672 especies de
aves (Bennett y Owens 1997) de las cuales el 11.5% están amenazadas de extinción (BirdLife
Internacional 2000). Cientos de estas especies pueden perderse si no se toman acciones de
conservación en forma inmediata (Sheppard 1995). Entre otras, las principales causas de
amenaza son la pérdida del hábitat, la fragmentación de las poblaciones y el comercio ilegal de
fauna silvestre (BirdLife International 2000).
Los grupos de aves en mayor peligro son aquellos que se trafican con fines de ornato,
además de aquellas especies con distribución muy restringida y/o hábitos muy especializados,
por ejemplo, los psitácidos (Ceballos 1993). Entre los psitácidos más amenazados se encuentra la
guacamaya roja (Ara macao) catalogada en el Apéndice I de CITES y por la IUCN como especie
con bajo riesgo. La guacamaya roja habita las selvas altas perennifolias, selvas medianas
subperennifolias, sabanas, áreas montañosas de baja altitud, asociándose a regiones ripárias de
grandes cuencas (Wiedenfeld 1994, Iñigo-Elías 1999). Wiedenfeld (1994) sugiere la existencia
de dos subespecies de guacamaya roja: Ara macao cyanoptera y A. m. macao. La primera esta
por ser considerada en peligro por la IUCN (Snyder et al. 2000).
La subespecie cyanoptera se distribuía desde el nivel del mar hasta los 500 metros. En
México se localizaba desde el sur de Tamaulipas, Veracruz, Oaxaca, Tabasco, Chiapas y
Campeche. En Centro América ocupaba todo Belice, a través de Guatemala hacia el sur,
Honduras, El Salvador, el centro de Nicaragua y una pequeña porción al norte de Costa Rica
(Wiedenfeld 1994, Juniper y Parr 1998). No obstante, ésta subespecie actualmente se distribuye
en poblaciones aisladas con un pequeño número de aves en la Selva Lacandona (Forshaw 1989,
Wiedenfeld 1994; aproximadamente 400 individuos, Iñigo-Elías 1996) y en Oaxaca (Wiedenfeld
1994; aproximadamente 50 individuos, Binford 1989), en los bosques del suroeste de Belice
(Wiedenfeld 1994; aproximadamente 200 individuos, Kainer 1991, Manzanero 1991), suroeste de
la región del Petén en Guatemala (Wiedenfeld 1994; se estiman entre 100 y 200 individuos,
Carreón-Arroyo e Iñigo 1998), noroeste de Honduras (Wiedenfeld 1994, no hay estimaciones del
tamaño poblacional) y el este de Nicaragua (Wiedenfeld 1994; población pequeña y aislada de
menos de 100 individuos, Martínez-Sánchez 1991). Wiedenfeld (1994) extrapoló, a partir del

24
número estimado de guacamayas rojas en Honduras, sugiriendo que la población total de A. m.
cyanoptera en México y Centroamérica es probablemente de 4000 individuos. Éstas se
encuentran en poblaciones altamente aisladas y pequeñas, su supervivencia a largo plazo parece
ser poco probable (Wiedenfeld 1994). En el 2001 se reunieron representantes de Belice,
Guatemala y México con la finalidad de definir un plan de acción y proteger a esta especie. Se
comentó que la población de guacamayas rojas en la Selva Maya está estimada en menos de 1000
individuos (Conservation International, 2001).
Las amenazas a las poblaciones de guacamaya roja son debidas a la destrucción del
hábitat, el comercio ilegal, la cacería de subsistencia, a la competencia por sitios de nidación por
abejas africanizadas, además de la fragmentación y el aislamiento de las poblaciones silvestres
(Wiedenfeld 1994, Iñigo-Elías 1999, CITES 2001). Entre otras, las causas de la fragmentación
del hábitat y de las poblaciones, pueden llevar a estas a la endogamia causada por flujo génico
restringido, convirtiéndose en un problema muy grave cuando las poblaciones son pequeñas y
aisladas (Wright 1921, Shonewald-Cox et al. 1983; Hedrick 2000).
Anualmente, las autoridades ambientales confiscan decenas de individuos, que en su
mayoría son objeto de tráfico ilegal de fauna silvestre. Por lo general se desconoce el sitio y
población de donde estas aves son originarias. Lamentablemente, muchos individuos mueren en
los lugares de confinamiento, o en el mejor de los casos son mantenidos en colecciones
zoológicas, reproduciéndolos sin el conocimiento del linaje al cual pertenecen.
Dada esta problemática, nosotros nos hemos planteado el objetivo de tratar de identificar
marcadores moleculares para las poblaciones silvestres de guacamaya roja (Ara macao
cyanoptera). Complementariamente, la obtención de datos moleculares nos permitirá evaluar la
variación genética dentro y entre poblaciones, identificar linajes silvestres en individuos cautivos
y proponer estrategias de manejo tanto de las poblaciones cautivas como silvestres de Ara macao
cyanoptera.
Materiales y métodos
Hasta la fecha, hemos colectado plumas de 51 individuos de guacamaya roja de cuatro sitios
geográficos tanto en México como en Centro América. Las localidades muestreadas son: Selva

25
Lacandona Chiapas, México (nueve muestras), Norte de Petén, Guatemala (23 muestras), zona de
la Mosquitia, Honduras (17 muestras) y Belice (dos muestras).
La extracción de ADN se realizó con el protocolo de Singer-Sam et al. (1989) a partir de
la pulpa de las plumas usando solución Chelex 5%. La amplificación y el aislamiento del
fragmento mitocondrial ND2 (522 pb) fueron realizadas por PCR en una termocicladora
GeneAmp PCR System 2400 (Perkin Elmer) con las condiciones siguientes: desnaturalización
por 20 s a 96 °C, hibridación por 20 s a 45 °C y extensión por 60 s a 71 °C, repitiendo esta
secuencia por un total de 35 ciclos. Alícuotas de 4 μl fueron evaluadas en electroforesis
horizontal en gel de agarosa al 2 %, los cuales se tiñeron durante 10 minutos en una solución de 2
pg/ml de bromuro de etidio y visualizados bajo luz UV. Las muestras positivas fueron purificadas
usando el kit GeneClean III (BIO 101, Inc.). Los purificados se secuenciaron usando el kit ABI
Prism Big Dye Terminator v 3.1 (Applied Biosystems) con las siguientes condiciones: 10 s a 95
°C, 5 s a 50 °C y 180 s a 60 °C por 32 ciclos. Estas amplificaciones fueron sometidas a limpieza
mediante columnas de Sephadex centrifugadas a 2,500 rpm durante 2 minutos. Los
electroferogramas se obtuvieron con una estación capilar de secuenciación ABI Prism 310
(Perkin Elmer). Las secuencias fueron editadas con el programa Sequencher versión 3.0 (Gene
Codes Corporation).
Los parámetros poblacionales fueron estimados con los programas Arlequín versión 2.0
(Schneider et al. 2000) y DnaSP versión 4.10.4 (Rozas et al. 2003). La variación intrapoblacional
fue determinada mediante los siguientes descriptores: diversidad nucleotídica π (Nei y Li 1979),
diversidad genética θ; la variación interpoblacional mediante el coeficiente de diversidad genética
GST (Nei 1987). Finalmente, estimamos el número de migrantes por generación bajo el modelo de
Slatkin (1991).
Complementariamente, se infirieron las interrelaciones de los individuos colectados por
medio de un análisis de máxima parsimonia. La reconstrucción se realizó usando el programa
PAUP* (Swofford 2002). Finalmente, con la ayuda del programa TCS 1.21 (Clement et al. 2000)
se ensambló una red de haplotipos. Dicha red nos permitió inferir el posible haplotipo ancestral, y
la vía más probable de diversificación y origen de nuevos haplotipos por medio de acumulación
de mutaciones puntuales.

26
Resultados
El análisis del alineamiento de las 51 secuencias del gen mitocondrial ND2 resolvió un total de
nueve haplotipos y once sitios segregados (Cuadro I.1). Todos los cambios observados
corresponden a transiciones, de las cuales cinco corresponden a cambios entre purinas (G – A) y
las seis restantes entre pirimidinas (T – C). Los haplotipos encontrados presentan la siguiente
distribución: siete en Guatemala, cinco en Honduras, tres en México y uno en Belice. El
haplotipo 02 (H02) fue el más frecuente encontrándose en las cuatro poblaciones, seguido por el
H01 que no ha sido registrado aún para la población de Belice (Figura I.1). Los datos obtenidos
nos revelaron la existencia de haplotipos únicos en tres de las poblaciones muestreadas. Para la
población de Guatemala se identificaron tres haplotipos exclusivos (H03, H04 y H05), para la
población de Honduras se encontraron igualmente tres haplotipos únicos (H06, H07 y H08),
mientras que para la población de Chiapas en México se registró un solo haplotipo endémico
(H09).
El análisis intrapoblacional mostró que los individuos colectados en Chiapas (México)
son los que presentaron la mayor variación genética (Cuadro I.2). La diversidad nucleotídica (π),
para las poblaciones que contienen más de un haplotipo, fluctuó dentro de un rango de 0.00316
(México) a 0.00187 (Honduras). De igual forma, con respecto al valor de θ este varió desde
1.05556 (México) hasta 0.68 (Honduras).
Las comparaciones interpoblacionales por el momento se limitan al coeficiente de
diferenciación genética (GST) y al número de migrantes por generación entre poblaciones (Nm).
El índice de diferenciación genética (Cuadro I.3) fue significativo entre las poblaciones de
Honduras y Guatemala (GST = 0.16, p = 0.007). Para el resto de las comparaciones, el valor de
GST no alcanzó significancia estadística. El nivel de flujo génico estimado fue elevado entre todas
las poblaciones. El menor flujo estimado se calculó entre las poblaciones de Honduras y Belice
(Nm = 1.22 individuos por generación), mientras que el flujo mayor fue entre México y
Honduras (Figura I.1).
Por medio del análisis de la red de haplotipos (Figura I.2) se observó que el H02 es el más
común y posee la probabilidad más alta de ser el haplotipo ancestral. Este haplotipo se comparte
entre las cuatro zonas muestreadas. Sin embargo, es más frecuente en la población de Chiapas
donde el 67 % de las muestras corresponden al H02. Los haplotipos específicos de la población

27
de Honduras (H06, H07 y H08) son más cercanos a H02. Por otro lado, los haplotipos H04 y H05
que se localizan exclusivamente en Guatemala se derivaron del H02 después de haber acumulado
una y dos mutaciones puntuales respectivamente. El tercer haplotipo endémico de Guatemala
(H03) es el resultado de una mutación del H01. Finalmente, la acumulación de tres mutaciones
por parte del H02 ha dado origen al haplotipo H09 que solo fue localizado en la población de
México.
La red de interrelaciones históricas entre individuos muestra una estructuración genética
moderada (GST = 0.0879, p = 0.041). Finalmente, se observa que las muestras se agrupan en dos
clados que no presentan una asociación geográfica determinada (Figura I.3).
Discusión
Aparentemente, el número de haplotipos encontrado por población está directamente relacionado
con el tamaño de muestra para cada localidad. Sin embargo los descriptores π y θ no
necesariamente siguen el mismo patrón. Los valores obtenidos para π y para θ indican que las
población de México, Honduras y Guatemala, son poblaciones demográficamente estables
(Carpenter et al. 2001).
El flujo génico permite la difusión de la variación genética entre las poblaciones y por lo
tanto uniformizándola para la especie. Tal como lo sugiere la regla de un migrante por generación
(Wang 2004) es probable que la variación interpoblacional calculada para A. m. cyanoptera este
disminuyendo. El alto flujo génico se infiere por los valores de GST negativos y los significativos
(Sinclair et al. 2001). Sin embargo, otros autores (Mills y Allendorf 1996) recomiendan
considerar ambas variaciones, intra e interpoblacional, ya que en muchas circunstancias un
migrante por generación no es suficiente para mantener una variación genética y producir
uniformidad en las frecuencias alélicas entre las subpoblaciones. Este número alto de migrantes
por generación también se ha visto en otros psitácidos. Wright y Wilkinson (2001) estimaron
para Amazona auropalliata, un valor de Nm superior a ocho. Si las secuencias no son agrupadas
por población y se evalúan de forma global π alcanza un valor de 0.0025. Este valor se considera
bajo especialmente si se compara con especies que se encuentran en peligro de extinción (p. e.
Pharomachrus mocinno, Solórzano et al., 2004). No obstante, hay que considerar que este valor
puede ser afectado por el reducido tamaño de muestra, pero particularmente es sensible a la

28
longitud de la región del genoma secuenciado. Por lo tanto estos valores deben ser corroborados
por medio de secuencias complementarias.
La presencia de haplotipos únicos y la frecuencia relativa por localidad de los haplotipos
ampliamente dispersos, pueden ser una herramienta para la identificación del origen geográfico
de los individuos decomisados o que se encuentren en cautiverio. Estos haplotipos únicos se
deben analizar para determinar si son unidades geográficas discretas o son un efecto del
muestreo.
La red de haplotipos sugiere que las diferentes poblaciones de Ara macao cyanoptera
presentan una reciente fragmentación. Esto se deduce por el número de acumulaciones de
mutaciones puntuales entre los haplotipos. Un rango de entre una a tres mutaciones se ha
apreciado en otras especies sometidas a presiones resultantes del efecto de la fragmentación
(Solórzano et al., 2004).
Conclusión
Aun cuando los datos presentados son preliminares es posible observar una tendencia en los
patrones de diversidad genética y estructuración poblacional. Los haplotipos descubiertos nos
pueden permitir iniciar un programa de monitoreo y manejo de ejemplares decomisados y en
cautiverio. Sin embargo es indispensable continuar con este estudio, aumentando el muestreo
tanto en poblaciones alternativas, como en muestras por población, y como en la longitud de las
secuencias de ADN.
Finalmente, la baja estructura histórica que presentan las poblaciones de la Guacamaya
roja es una evidencia alternativa que corrobora el hecho de que la fragmentación del habitad es
un evento reciente. Por lo tanto es posible que esta pérdida de hábitat actual no haya generado un
efecto irreversible en la variabilidad genética de esta especie. La estrategia sugerida con este
trabajo es preservar áreas grandes con poblaciones sustentables y proveer el movimiento de
individuos entre éstas áreas. A este respecto la propuesta de mantener un corredor
mesoamericano permitiría el mantenimiento genético de estabilidad de la dinámica poblacional
de Ara macao cyanoptera.

29
Agradecimientos
Este trabajo ha sido posible gracias al apoyo de la Comunidad Lacandona, del Ejido Reforma
Agraria, de la Comisión Nacional de Áreas Naturales Protegidas (CONANP), del Zoológico
Miguel Álvarez del Toro Instituto de Historia Natural, todos estos en el Estado de Chiapas,
México. De igual forma queremos dar nuestro reconocimiento a la Comisión Nacional de Áreas
Protegidas, Wildlife Conservation Society, Aviarios Mariana en Guatemala y al Parque Montaña
Guacamaya en Honduras. El trabajo de campo y laboratorio ha sido financiado por el Programa
de Apoyo a Investigación en Ciencia Básica del Consejo Nacional de Ciencia y Tecnología
(CONACyT, proyecto 35202-V). LMGF cuenta con el apoyo de una beca de estudios doctorales
otorgada por CONACyT.
Literatura citada
Bennett P. M., Owens I. P. F. 1997. Variation in extinction risk among birds: Chance or
evolutionary predisposition? Proceedings of the Royal Society of London Series B
Biological Sciences 264, 401-408.
Binford L. C. 1989. A distributional survey of the birds of the Mexican State of Oaxaca.
Ornithological Monographs 43, 99-100.
Birdlife International. 2000. Threatened birds of the world. The official source for birds on the
IUCN Red List. Barcelona and Cambridge, UK: Lynx Editions and BirdLife International.
Carpenter D.W., Jung R.E., Sites J.W. Jr. 2001. Conservation genetics of the endangered
Shenandoah salamander (Plethodon shenandoah, Plethodontidae). Animal Conservation
4, 111-119.
Carreón-Arroyo G., Iñigo Elías E. E. 1998. Reporte y estrategia del taller trinacional para la
conservación y recuperación de la guacamaya escarlata (Ara macao) en la Selva Maya.
San Cristóbal de las Casas, Chiapas, México. Del 28 al 30 de septiembre de 1998.
Ceballos G. 1993. Especies en peligro de extinción. Ciencias. No. Especial 7.
CITES. 2001. Guacamaya Roja (Ara macao). Información recopilada del taller trinacional
Belice-Guatemala-México, de la revisión de literatura científica, información
proporcionada por algunos gobiernos y comentarios de expertos. México, mayo 2001.

30
Clement M., Posada D., Crandall K. A. 2000. TCS: a computer program to estimate gene
genealogies. Molecular Ecology 9, 1657-1660.
Conservation Internacional. 2001. Comunicado de prensa. Guacamaya roja en grave peligro de
extinción. “Guacamayas sin fronteras última oportunidad para conservarlas” Estación
Chajul, Chiapas, del 9 al 13 de Febrero de 2001.
Ehrlich P., Ehrlich A. 1981. Extinctions. Random House, San Francisco, USA.
Forshaw J.M. 1989. Parrots of the World. Third Edition. Melbourne.
Hedrick P. W. 2000. Genetics of populations. Second edition. Jones and Bartlett Publishers.
Sudbury, Massachusetts.
Iñigo-Elias E. E., 1996. Ecology and breeding biology of the Scarlet Macaw (Ara macao) in the
Usumacinta Drainage Basin of México and Guatemala. Ph.D. Dissertation. University of
Florida. Gainesville, Florida, USA. 117 pp.
Iñigo Elías E. E. 1999. Las guacamayas verde y escarlata en México. Biodiversitas 5, 7-11.
Juniper T., Parr M. 1998. Parrots. A guide to the parrots of the World. Pica Press, Sussex. 584
pp.
Kainer M. 1991. Conservation of the Scarlet Macaw (Ara macao): subtropical moist forest life
zone, Belize, Central America. En: Proceedings of the First Mesoamerican Workshop on
the Conservation and Management of Macaws. Jack Clinton-Eitniear, ed. Center for the
Study of Tropical Birds, Inc. San Antonio, Texas, USA, pp. 5-10.
Manzanero R., 1991. The Status of the Scarlet Macaw (Ara macao) Belize, Central America. En:
Proceedings of the First Mesoamerican Workshop on the Conservation and Management
of Macaws. Jack Clinton-Eitniear, ed. Center for the Study of Tropical Birds, Inc. San
Antonio, Texas, USA, pp. 11
Martinez-Sanchez J. C., 1991. Distributional and conservation of macaws in Nicaragua. En:
Proceedings of the First Mesoamerican Workshop on the Conservation and Management
of Macaws. Jack Clinton-Eitniear, ed. Center for the Study of Tropical Birds, Inc. San
Antonio, Texas, USA pp 19-22.
Mills L. S., Allendorf F. W. 1996. The one-migrant-per-generation rule in conservation and
management. Conservation Biology 10, 1509-1518.
Nei M. 1987. Molecular evolutionary genetics. New York: Columbia University Press.

31
Nei M., Li W. H. 1979. Mathematical model for studying genetic variation in terms of restriction
endonucleases. Proceedings of National Academic of Science 76, 5269-5273.
Rozas J., Sánchez-DelBarrio J.C., Messenger X., Rozas R. 2003. DnaSP, DNA polymorphism
analyses by the coalescent and other methods. Bioinformatics 19, 2496-2497.
Schneider S., Roessli D., Excoffier L. 2000. Arlequín Ver 2.0. A software for population genetics
data analysis. http://anthropologie.unige.ch/arlequin/
Sheppard. 1995. Captive propagation and avian conservation. Pp 227-240, en: Conservation of
endangered species in captivity. Gibbons E. Jr., Durrant B., Demarest J. (Eds.). State
University of New York Press, Albany.
Shonewald-Cox C. M., Chambers S. M., MacBryde B., Thomas W. L. 1983. Genetics and
conservation: a reference for managing wild animals and plants populations.
Benjamin/Cummings. Melo Park, California.
Sinclair E.A., Swenson E.L., Wolfe M.L., Choate D. C., Bates B., Crandall K.A. 2001. Gene
flow estimates in Utah´s cougars imply management beyond Utah. Animal Conservation
4, 257-264.
Singer-Sam J., Tanguay R. L., Riggs A. D. 1989. Use of Chelex to improbe PCR signals from a
small number of cells. Amplifications (a forum for PCR users) 3, 11.
Slatkin M. 1991. Inbreeding coefficients and coalescence times. Gen. Res. Camb. 58, 167-175.
Snyder N., McGowan, P., Gilardi, J., Grajal, A. (eds.). 2000. Parrots. Status Survey and
Conservation Action Plan 2000–2004. IUCN, Gland, Switzerland and Cambridge, UK.
Solórzano S., Baker A. J., Oyama K. 2004. Conservation priorities for resplendent quetzals
based on analysis of mitochondrial DNA control region sequences. The Condor 106, 449-
456.
Swoffrod D. L. 2002. PAUP*: Phylogenetic Analysis Using Parsimony (*and other methods) v
4.0b10. Sinauer Associates, Sunderland Massachusetts.
Wang J. 2004. Application of the one-migrant-per–generation rule to conservation and
management. Conservation Biology 18, 332-343.
Wiedenfeld D. A. 1994. A new subspecies of scarlet macaw and its status and conservation.
Ornitología Neotropical 5, 99-104.
Wright S. 1921. Systems of mating. Genetics 6, 111-178.

32
Wright T.F., Wilkinson G.S. 2001. Population genetic structure and vocal dialects in an amazon
parrot. Proceeding of Royal Society of London Serie B 268, 609-616.

33
Cuadro I.1. Listado de haplotipos y sitios segregados. Los números se refieren a la posición del
sitio segregado dentro de la secuencia.
0 0 0 1 1 2 2 2 3 3 3
4 6 9 0 5 0 6 9 1 4 5
6 8 7 7 1 5 2 3 6 1 5
Haplotipo 01 (H01) A T C A T C G T A C C
Haplotipo 02 (H02) . . . . . T . . . . .
Haplotipo 03 (H03) . . . . C . . . . . .
Haplotipo 04 (H04) . . . . . T . . . T .
Haplotipo 05 (H05) . . . . . T A . G . .
Haplotipo 06 (H06) . . . . . T . . . . T
Haplotipo 07 (H07) . . . . . T . G . . .
Haplotipo 08 (H08) . C . . . T . . . . .
Haplotipo 09 (H09) G . T G . T . . . . .
Cuadro I.2. Descriptores de la variabilidad genética para las cuatro poblaciones geográficas de
Ara macao cyanoptera. Número de muestras (n), número de haplotipos (H), diversidad
nucleotídica (π), diversidad genética (θ), y desviación estándar de θ (SD θ).
Población n H θ SDθ
Guatemala 23 5 0.00243 0.86561 0.70527
Honduras 17 5 0.00187 0.67647 0.60762
México 9 3 0.00316 1.05556 0.87157
Belice 2 1 0.00000 0.00000 0.00000

34
Cuadro I.3. Índice de fijación genética GST entre cuatro poblaciones de Ara macao cyanoptera.
Por arriba de la diagonal se presentan los valores de significancia p. Por debajo de la diagonal se
muestran los valores de GST.
Guatemala Honduras Belice México
Guatemala * 0.0072 0.5283 0.1168
Honduras 0.1609 * 1 0.4434
Belice 0.0641 -0.2904 * 1
México 0.0666 0.0006 -0.2714 *

35
Figura I.1. Frecuencias y distribución de haplotipos en las cuatro poblaciones geográficas
muestreadas para Ara macao cyanoptera. Los números en las líneas que conectan a los pares
poblacionales representan los valores de individuos migrantes por generación (Nm) estimados a
partir de los valores de GST.

36
Figura I.2. Distribución y red de haplotipos para el gen mitocondrial de ND2. El área de los
círculos es directamente proporcional a el numero de poblaciones en que se encuentra el
haplotipo (H) correspondiente. Los números en las líneas indican las mutaciones puntuales y su
posición en el segmento secuenciado.

37
Figura I.3. Árbol más parsimonioso que muestra las interrelaciones históricas entre los 51
individuos secuenciados para el gen mitocondrial ND2. Las etiquetas representan el sitio de
origen del individuo: Belice (B), México (CH), Guatemala (G), y Honduras (H).

38

39
CAPÍTULO II
THE EFFECT OF THE MAYAN FOREST FRAGMENTATION ON THE GENETIC
STRUCTURE OF THE MESOAMERICAN SCARLET MACAW (Ara macao cyanoptera)
García-Feria, Luis Manuel and Alejandro Espinosa de los Monteros
Sometido a Biological Conservation. Número asignado: BIOC-D-08-00943

40

41
Abstract
The Mesoamerican scarlet macaw (Ara macao cyanoptera) is one of the most fragile lineages of
New-World psittacids. Estimates concur that there are nearly 1 000 wild individuals, which are
segregated in small tropical-forest fragments. Its population decline is the result of nest-site
competition with African bees, illegal capture, and habitat deforestation. For this study we
evaluated the genetic variation in the Mesoamerican populations, identified genetic markers that
might be used for future reintroductions, and assessed the effect of habitat fragmentation on the
genetic structure of this bird. The analyses were based on DNA sequences from two
mitochondrial (ND2, and ND5), and one nuclear fragments (RAG-1). We identified 26 different
haplotypes of which 24 were restricted geographically; thus the populations contain higher levels
of genetic variation than other bird species living under similar conditions. The genealogy
showed no historical structure among the populations, supporting the idea that they represent a
cohesive reproductive unit that is maintained by relatively restricted gene flow. Our results
revealed different demographic patterns. The populations from Belize and Guatemala have been
in stasis, whereas the remaining population has suffered events of genetic expansion. We
inferred that such expansion events took place between 50 000 and 36 000 years ago during the
Pleistocene’s tectonic activity, along with harsh environmental changes, might be responsible for
favoring the processes of differentiation that led to the origin of endemic haplotypes. Apparently,
the current fragmentation of the Mayan forest has not yet impacted irreversibly the genetic stock
of this macaw
Key Words: Ara macao, scarlet macaw, fragmentation, genetic markers, Mayan forest,
phylogeography.

42
1. Introduction
The Scarlet Macaw (Ara macao) is the third largest of the16 macaws species currently
recognized (Sibley and Monroe, 1990). It is found from sea level to 600 m in mountainous zones
covered by humid forest associated to water bodies such as lakes and rivers (Iñigo-Elías, 1996,
1999). The species had a discontinuous distribution from Mexico to Brazil, with a gap in Panama
(Forshaw, 1989; Juniper and Parr, 1998). Habitat degradation, however, has confined the current
population to small patches of the forest. For this reason CITES has identified this macaw as an
endangered species (Sánchez et al., 1998), whereas the UICN has declared it as a species in risk.
The scarlet macaw is a polytypic taxon, which encompasses two subspecies (i.e., A. m.
cyanoptera and A. m. macao; Wiedenfeld, 1994).
The Mesoamerican scarlet macaw (A. m. cyanoptera) was found historically in Mexico
(i.e., Tamaulipas, Veracruz, Tabasco, Campeche, Oaxaca, and Chiapas), Belize, Guatemala,
Honduras, El Salvador, and Nicaragua (Juniper and Parr, 1998). During the past 50 years this
subspecies has been wiped out from over 90% of its original distribution (Thurber et al., 1987;
Wiedenfeld, 1994). The entire Mesoamerican population has been estimated in 4 000 individuals
(Wiedenfeld, 1994). Currently, there are populations in Oaxaca (Chimalapas; Binford, 1989),
Chiapas (Lacandonian forest; Macias et al., 2000), Belize (Upper Macal and Raspaculo River;
Vaughan et al, 2006), Guatemala (Peten; Pérez-Pérez, 1998; Renton, 2000), Honduras (Rio
Plátano Biosphere Reserve; Thorn, 1991; Renton, 2000), and Nicaragua (Cosigüina; Martínez-
Sánchez, 1991). Even though the species is protected, its populations is still declining and the
current number of individuals in the wild are estimated in 1 000, and divided in relict colonies
between 50 to 400 birds (Partners in Flight, 2001). Most of these populations inhabit in patches
of tropical forest located within what is commonly known as the Mayan Forest. The main threats
to the wild population are habitat degradation (Sheppard, 1995), hunting, nest displacement by
African bees, and illegal capture for pet trade (BirdLife International, 2000; Snyder et al., 2000;
CITES, 2001).
Extinction is the ultimate problem in conservation biology. Catastrophic events,
demographic, and genetic problems are factors that facilitate natural extinction in the wild
(Ewens et al., 1987; Soulé, 1987; Lande, 1988). Endogamy due to restricted genetic flow and
genetic drift in very small populations are the main issues among the genetic factors (Wright,

43
1921; Shonewald-Cox et al., 1983; Hedrick, 2000). One of the central objectives of conservation
genetics is to understand the relationship between genetic diversity and population viability.
Although high levels of genetic variation are not necessary a requisite to ensure the survival of a
species, low levels of genetic variation correlate with physiological abnormalities like poor sperm
quality and higher vulnerability to viral infections (O’Brien et al., 1985; Yuhki and O’Brien,
1990). Population genetics infers the amount of genetic variation within and among populations.
Based on these data it is possible to estimate gene flow, genetic drift, breeding systems, mutation
rate, and selection coefficients (Templeton et al., 1995; Hedrick, 2000). Additionally,
phylogeographic analyses allow us to understand how the genetic variation is structured in space
and time (Avise, 2000). This kind of analysis has been used to assess genetic structure in order to
evaluate the effect of habitat fragmentation and conservation strategies (Lovette et al., 1999;
Newton et al., 1999; Templeton, 1998, 2001; Fuerst and Austin, 2004).
Fragmentation followed by complete or nearly complete genetic isolation can create close
associations between haplotypes and geography. Sometimes genetic isolation causes that
fragmented populations behave as separate species, but with geography acting as the only barrier
to gene flow (Wright and Wilkinson, 2001). In such cases the haplotype trees recover an
historical structure that is correlated with the distribution of the lineages. Furthermore, the
relationship between the isolation time due to fragmentation and the time scale of the coalescent
process can produce several historical patterns. For example, if the fragmentation event last
longer than the coalescent time, the haplotype tree will develop monophyletic clades that mark
the isolates (Templeton, 2001).
The goal of the present study was to evaluate the genetic variation within and between
populations of A. m. cyanoptera, and to assess the potential effect of demographic isolation and
the habitat fragmentation on these populations. The molecular data let us to infer patterns of
population genetic structure and gene flow. Identifying wild geographic lineages can be used for
assigning putative places of origin of captive or seized specimens. Finally, the understanding of
such matters can be used in deciding conservation priorities, and for outlining management
programs such as translocation or breeding strategies for captive birds.
2. Materials and methods

44
2.1. DNA samples
Feather samples were obtained from six wild populations of Ara macao cyanoptera in Mexico,
Belize, Guatemala and Honduras (Fig. II.1). The precise coordinates of the localities where
populations are found have been deliberately omitted from this paper, in order to discourage
indiscriminate collecting of this endangered species for commercial purposes. Chiapas I
(Reforma Agraria) is located in the area of Marqués de Comillas close to the Lacantún River at
the east edge of Montes Azules Biosphere Reserve. Chiapas II (Democracia) is located in the area
of Maravilla Tenejapa between the rivers Lacantún and Jataté close to the west edge of Montes
Azules Biosphere Reserve. The site Guatemala I (Peñón de Buenavista) is located in the Laguna
del Tigre National Park. The samples assigned to the population Guatemala II were collected at
the Petén zone. The population from Belize inhabits the Central Mayan Mountains. The site from
Honduras (Mosquitia) is located at the Río Pátuca National Park. We obtained from two to 16
feathers samples at each site. These samples were collected at the base of tree where the macaw
rest, nest or feed. The collected feathers were stored in 90% ethanol or lysis buffer for their
transport to the laboratory.
For this study we sequenced two mitochondrial markers and one nuclear. The
mitochondrial NADH dehydrogenase subunit 2 (ND2) was amplified using the primers L5215:
5’-tatcgggcccataccccgaaaat-3’ and H5578: 5’-ccttgaagcacttctgggaatcaga-3’, which provide the
first 362 bp of this gene (Hackett 1996). Another 337 bp, belonging to the central region of the
NADH dehydrogenase subunit 5 (ND5) were amplified with the primers L13589: 5’-
ccagcagcaatagaaggccc-3’ and H14149: 5’-cctattttgcggatgtcttgttc-3’. Two sets of primers (R13-
R16 and R11-R12b) were used to amplify and sequence 861 bp of the nuclear recombination-
activating gene 1 (RAG-1). These and additional sets of primers for the RAG-1 gene were
described in Groth and Barrowclough (1999). The molecular matrix included 1 561 bp for each
of 55 wild individuals.
The proximal tip of the feather calamus was ground in Chelex 5% (w/v solution) for total
genomic DNA extraction following the method suggested by Singer-Sam et al. (1989). DNA
amplification was conducted in a Peltier-effect thermocycler (ABI GeneAmp PCR system 2400).
The thermocycling procedure for the mitochondrial genes consisted of one initial denaturing step
at 95º C for 120 s, followed by 35 cycles of 95º C for 20 s, 50º C for 20 s, and 74º C for 90 s;

45
with one final cycle at 74º C for 180 s. For the nuclear RAG-1 we used a modified hot-start
touchdown PCR, with an initial denaturing step at 94° C for 10 min, followed by five cycles of
95° C for 20 s, 61° C for 20 s, 72° C for 60 s. This was followed by two identical 5-cycle phases,
with a 2° C reduction in annealing temperature for each phase. The final phase consisted of 25
additional cycles identical to the preceding cycles, but with a 55° C annealing temperature (40
total cycles). All PCR reactions were conducted along with positive and negative controls to
detect potential false positives due to contamination. Successful amplifications were purified
using the GeneClean III kit (BIO 101 Inc.). Purified PCR products were subjected to cycle
sequencing using the ABI Prism BigDye® Terminator v3.1 Cycle Sequencing Kit, following the
protocol suggested in the kit instructions. The excess of Taq dideoxy terminators was removed
with Centri-Sep™ spin columns (Princeton Separations) in a variable speed microcentrifuge at 2
500 rpm for 2 min. Final purifications were dried down in a vacuum centrifuge and suspended in
25 µl of the loading solution. Sequencing products were subjected to capillary electrophoresis in
the ABI Prism 310 DNA Sequencer (Perkin Elmer). Sequence files were analyzed with the aid of
the program Sequencher v 3.0 (Gene Codes Corp., Ann Arbor, MI). Fragments were sequenced
on both DNA strands to ensure accurate data collection. All sequences have been deposited in
GenBank under the following inclusive accession numbers: XXXXXXXX-YYYYYYYY. (Los
números de acceso estarán disponibles al momento de la aceptación del manuscrito).
2.2. Genetic analyses
The genetic variation within and among populations was evaluated using empiric descriptive
values such as genetic diversity index (), haplotype diversity (h), nucleotide diversity (π) (Nei
and Li, 1979), and segregating sites (S) (Nei and Kumar, 2000). The fraction of the genetic
variation distributed among populations was estimated using Fst statistic (Lynch and Crease,
1990). A total of 1001000 permutations were run to estimate Fst and its significance level.
Population stasis was evaluated using the raggedness statistic (r) (Harpending, 1994) and R2
(Ramos-Onsins and Rozas, 2002). From the Fst and we were able to estimate gene flow (Nm;
Slatkin, 1991) and the effective population size (Ne) respectively. The mismatch distribution was
used for testing the hypothesis of population expansion (Rogers and Harpending, 1992). Finally,
we computed the historical parameter of population change since the most common ancestor (;

46
Rogers and Harpending, 1992). The calculations of all the above descriptors were performed with
the aid of the computer programs DNASP ver. 4.10.4 (Rozas et al., 2003), and Arlequin ver. 3.0
(Excoffier et al., 2005).
Haplotype interrelationships were inferred based on Bayesian analyses (Huelsenbeck et
al., 2002). The computer program Modeltest 3.04 (Posada and Crandall, 1998) was implemented
to statistically compare successively nested models, and to determine the appropriate model of
sequence evolution for the data set. The selected model corresponded to the HKY for the ND2
and RAG-1 genes, whereas for the ND5 was HKY + I. Trees were generated with MrBayes 3.0
(Huelsenbeck and Ronquist, 2001; Ronquist and Huelsenbeck, 2003) using Markov chain Monte
Carlo simulations with the Metropolis-Hasting algorithm. The search was run for 10 million
generations, with four parallel chains and sampling every 100th
generation. The burn-in value was
set when –lnL scores reached an asymptote. A majority-rule consensus tree after burn-in was
used to estimate the posterior probabilities for each node. Amazona farinosa (Eberhard and
Bermingham, 2004; Tavares et al., 2006), A. xanthops (Tavares et al., 2006), Ara ararauna
(Tavares et al., 2006), Ara militaris were employed as outgroups for rooting the phylogenetic
tree. Finally, a minimum–spanning network (parsimony based) for the haplotypes was inferred as
an alternative to the Bayesian trees. This network was recovered using the program TCS v. 1.21
(Clement et al., 2000).
3. Results
3.1. DNA polymorphism
A potential source of error for this kind of analysis is the presence of pseudogenes that originated
as translocated fragments from other genome regions. Evidence that the sequences used for this
study belong to the functional genes is as follows. Tavares et al. (2006) observed for other
species of parrots a similar pattern for the G-C proportion in their DNA. The sequence translation
did not result in nonsense codons for the protein coding regions or apparent frame shifts. Also,
the data set did not show major discrepancies compared to those deposited in the GenBank for
psittacidae. Finally, there was no evidence of heteroplasmy in the sequences of either
mitochondrial gene.

47
The ND2 region included the sequences for the tRNA-Met (48 bp), and the first 113 aa
residues of the NADH dehydrogenase subunit 2 that represents the first third at the 5’ end of this
gene. The G-C composition in this fragment was 46%. This region had 11 variable sites from
which one was a transversion from thymine to guanine, whereas the other 10 sites were
transitions (T-C = 6, G-A = 4; Table II.1). A total of nine different haplotypes were recovered
from the ND2 sequences. The haplotype diversity was 0.6150, whereas the nucleotide diversity
was 0.0023. The second mitochondrial fragment selected for this study coded for 112 aa in the
middle section of the ND5 gene. The G-C composition (47%) was similar to the ND2 sequence.
This second locus encompassed eight variable sites that were responsible for producing nine
haplotypes. We detected five transitions from thymine to cytosine, two from guanine to adenine,
and one transversion from cytosine to adenine. The molecular diversity was 0.2720 and 0.0012
for h and respectively. In spite of its length (861 bp) the nuclear partition had the lowest
variation. The RAG-1 sequences coded for the first 297 aa, and had a G-C composition of 40%.
We observed twelve segregating sites from which one was a transversion (A to C) and eleven
were transitions (T-C = 7, G-A = 4; Table II.1). From this fragment we recovered twelve
different haplotypes. Such variation accounted for an h value of 0.4450, and a value of 0.0007.
A total of 26 haplotypes were obtained after combining the three DNA fragments (S = 31,
h = 0.8148, = 0.0012; Table II.2). From these, 23 haplotypes were singletons (unique
haplotypes). One singleton was recorded in Belize, four in Chiapas I, two in Chiapas II, two in
Guatemala I, six in Guatemala II, and eight in Honduras (Table II.1). Haplotype 09 was the most
common and widespread haplotype (Fig. II.2 and Fig. II.3). We registered this haplotype in 23
individuals and it was only absent from Guatemala II. Haplotype 06 was the second most
common, and was sampled in Chiapas I, and in both Guatemalan sites (Fig. II.2 and Fig. II.3).
3.2. Genealogical and population inferences
The haplotype interrelationships tree (Fig. II.2) corroborates the monophyly of the scarlet macaw
with a clade posterior probability support value of 72%. This clade is characterized by six
unambiguous molecular synapomorphies in the ND2 gene [position 94 (C), 151 (T), 262 (G), 295
(T), 325 (T) and 334 (C)]; five in the ND5 gene [position 20 (C), 76 (T), 124 (T), 196 (T) and
313 (A)]; and three in the RAG-1 gene [position 152 (G), 489 (A) and 726 (T)]. We recovered

48
two minor subclades within the Mesoamerican scarlet macaw. Haplotypes 08, 11, 13, and 23
were encompassed within the first subclade. Apparently, there was no congruence between the
haplotypes and their geographical distribution. We collected these four haplotypes in Belize,
Honduras, and Chiapas. The second subclade scored a high clade posterior probability (95%). It
was formed by haplotypes 18 and 21 that were collected in Honduras. The remaining 20
haplotypes were recovered as single terminal units forming a basal polytomy. Therefore, no
cladistic structure was recovered within the Mesoamerican scarlet macaw. This was expected for
haplotypes belonging to a cohesive evolutionary unit (i.e., species).
The number of segregated sites observed within each population was highly variable,
ranging from two to 12 variable nucleotide positions (Table II.2). The estimated value for
nucleotide diversity within populations was low (Table II.2). The highest nucleotide diversity
was found in Chiapas I ( = 0.0014; S = 8). This locality had two times the nucleotide diversity
calculated for Guatemala I ( = 0.0007; S = 7). In general, the number of haplotypes discovered
within populations ranged from two to ten (Table II.2). Haplotype diversity was highly variable,
where the highest value estimated in the samples was found in the population from the
Guatemala II (h = 0.9643; H = 7). Whereas the lowest haplotype diversity was recorded in
Guatemala I (h = 0.4670) where only four haplotypes were found in 15 sampled individuals. A
correlation between sample size and number of haplotypes returned a correlation value of r2 =
0.6; therefore, there was no clear effect associated with haplotype discover. Levels of variation
among the six populations suggested different recent histories (Table II.2). The R2 statistic was
significant for Chiapas I, Chiapas II, Guatemala II, and Honduras, suggesting slow but
continuous population growth. The values of this parameter for the rest of the populations were
more consistent with those of stable populations. Finally, the shape of mismatch distributions
(Fig. II.4) corroborated the results obtained with R2 statistic for population growth.
The AMOVA test revealed that nearly 91% of the molecular variance occurred within
populations, whereas the remaining 9% was explained by genetic differences among populations
(Table II.3). Pairwise population values for FST revealed small but significant genetic
differentiation of Guatemala II with respect to the other Central American sites (Table II.4).
Chiapas I also showed significant genetic fixation with respect to Guatemala I and Honduras.
Estimates of gene flow between populations were extremely variable, ranging from 1.23 to an
infinite interchange of individuals per generation (Table II.4).

49
4. Discussion and conclusions
4.1. Recent population history
Coalescent theory states that rare haplotypes have a high probability of being recently derived,
and that older haplotypes should be more widespread than younger haplotypes (Templeton,
1998). Thus, haplotype 09 could be considered as the ancestral since it was observed in 33% of
specimens and was missing only from Guatemala II (Table II.1). Similarly, the population from
Honduras showed the highest genetic diversity and number of haplotypes, suggesting its probably
ancestral condition. Following this idea, the invasion path within Mesoamerica began in Central
America continuing toward the north into Mexico. The small fraction of the genetic variation
observed among populations (i.e. 9%; Table II.3) corroborates a highly cohesive reproductive
unit for the Mesoamerican scarlet macaw. The molecular data suggest that restricted gene flow by
long distance dispersal could be maintaining cohesion between the populations (Table II.4).
However, the absence of continuous distribution of the vegetation makes the existence of a
contemporary gene flow among the Mayan forest patches a difficult event. Some medium size
psittacines (i.e., Amazona farinosa) fly 143 km in linear distance, and have a home range of 300
km2 (Bjork 2004). However, Carreón (2000) measured a home range of 60 km
2 and a mean
dispersion range of 16 km for a population of scarlet macaw in Montes Azules. The significant
geographic separation, as well as the widespread distribution of Haplotype 09, could be also
explained by human translocation. In fact, translocation can be an ordinary outcome for a species
like the scarlet macaw that has been subjected for many decades to continuous trade as exotic pet
and zoo specimen.
The lack of phylogenetic structure between the populations made impossible to recover
general geographic markers for individual sites. Perhaps, the use of alternative molecular sources
(e.g., microsatellites) with higher mutation rate than the ones used here might identify such
geographic markers. Nonetheless, the relatively high genetic diversity within each population let
us to identify regional or local haplotypes. Therefore, they represent genetic landmarks for their
particular populations (Table II.1). Local molecular markers like those observed in this study are
of great value for identifying the appropriate haplotypes for safely repopulating a specific area, or
for attempting liberation programs of captive birds.

50
Glenn and Avise (1998) estimated a mutation rate of 2% in mitochondrial loci for
different vertebrate taxa. Considering the genetic diversity index (θ; Table II.2), and assuming
that such a mutation rate holds for the mitochondrial partitions of the Mesoamerican scarlet
macaw it is possible to estimate its effective population size (Ne). The smallest Ne was estimated
for Chiapas II with 24 individuals, whereas the largest Ne was computed for Honduras with 60
individuals (Table II.2). For the remaining sites an average Ne of 42 (± 9) was estimated. There is
no doubt that these numbers corroborate the delicate situation of the Mesoamerican populations
of this species. Nonetheless, the small mutational distances along with an excess of rare alleles
were consistent with events of recent demographic expansion. At least that was a reliable
conclusion for four populations. These demographic expansions can be dated based on the values
obtained for (Table II.2). This estimator indicates the time to the most common recent ancestor
in terms of mutational units. Once again, using the 2% mutation rate estimated by Glenn and
Avise (1998) we computed the absolute time since these demographic expansions. The oldest
expansion took place in Guatemala II approximately 52 000 years ago, whereas the most recent
happened nearly 36 000 years ago in Chiapas II, which coincide with an intensive tectonic
activity and harsh environmental changes during the Pleistocene in Mesoamerica (Behrensmeyer
et al., 1992). Variations in the amplitude of glacial cycles during this period resulted in a climatic
history that was neither simple nor directional. Tropical ecosystems went through periods of
contraction during glacial times, followed by periods of expansion during interglacial times
(Street, 1981). These fluctuations produced changes altering the dispersion pattern and gene flow
of many terrestrial species, therefore favoring the processes of differentiation that led to the
origin of endemic haplotypes (Avise et al., 1998). Others phylogeographic analyses in
Mesoamerica are needed in order to assess phylogeographical concordance, and to understand the
historical and ecological dynamics of the scarlet macaw populations.
4.2. Mayan Forest fragmentation
Although the molecular data supports patterns of demographic expansion or at least demographic
stasis, the high deforestation rate is definitely threatening the Mesoamerican scarlet macaw. The
recent alteration history of the Mayan forest is complex. Nearly 4 500 years ago the Mayans
began the occupation of Mesoamerica in the north region of Petén (Guatemala), and reached the

51
highest development 1 400 years ago (Palerm, 1972). During this time the Mayan forest was
highly populated, with an extensive trade system of amber, cacao, vanilla, fur, and feathers. The
fall of the Mayan civilization took place around the year 1 200 due to war, overpopulation,
weather change, and ecological alteration (Duvenger, 1999). Álvarez del Toro (1985)
documented the status of the Mayan forest throughout the first half of the XX century. He
mentions that in 1945 the Lacandon Forest was a pristine ecosystem, and large populations of
scarlet macaws could be found in the areas of Marqués de Comillas, and Jataté River. Forty years
latter only a few individuals of this bird could be observed due to the rapid deforestation resulted
from human colonization (Álvarez del Toro, 1985). Currently, the macaw population at this area
has been wiped out by the transformation of the forest for agriculture and cattle rising. The
Mayan forest is going throughout a global alteration. In this area, human population growth rate
increments in 4.5% each year. The consequences of this are forest destruction, soil erosion, water
pollution, and wild life extinction. Mesoamerica has one of the highest deforestation rates in the
world. During the 1980’s the deforestation rate in Belize was 0.2%, 1% in the Lacandon Forest
and in Guatemala was 1.7% per year. Toward the year 2000 these rates have increased in average
3%. Between 1990 and 1995 nearly 500 000 hectares were lost due to uncontrolled fire from
agricultural activities. In 1998 2.5 million hectares were lost in Central America. Conservation
International (2004) has identified the Lacandon Forest (Mexico) and Laguna del Tigre National
Park (Guatemala) as the most affected areas. One more source of forest fragmentation is the
building of dams. The water flow of the Usumacinta River in the Lacandon Forest has been
altered destroying important areas covered with tropical forest (Conservation International,
2004). Similar projects are taking place in the Chiquibul National Park (Belize), a dam build in
the Chalillo River flooded 800 hectares of Mayan forest (Ankersen and Arriola, 2001). Marqués
de Comillas (Chiapas) and Laguna del Tigre (Guatemala) undergo a sustained destruction due to
oil extraction (Conservation International, 2004). The construction of highways and other
communication roads are also a serious threat. The highway connecting El Naranjo in Guatemala
to the Mexican border has allowed over 2 500 settlements that affect the Mayan forest (Ankersen
and Arriola, 2001). Further forest fragmentation is resulted by the construction of a highway that
connects the archaeological zones of Tikal (Guatemala) and Calakmul (México).
Apparently, the genetic stock observed in the Mesoamerican scarlet macaw has not been
irreversibly affected by the rampant destruction of the Mayan forest that has occurred during the

52
last 60 years. This is probably due to the genetic buffer produced 50 000 years ago throughout the
population expansion as inferred by the molecular data. There has been, however, an alarming
reduction in the number of wild bird. Special attention should be given to the Mesoamerican
population that remains in this severely fragmented and degraded forest (Wiedenfeld 1994). The
ongoing extraction of birds and habitat destruction will result in the rapid loss of endemic
haplotypes, and the subsequent extinction of the Mesoamerican scarlet macaw (e.g., population
from El Salvador). We are confident that this lineage still has the self-possibility for recovering in
its wild habitat. This would be only possible, however, if the ongoing processes leading to
decline of the species are stop immediately. The conditions of the Mayan forest must be
constantly surveyed to preserve a suitable habitat that can support a healthy population of
macaws. The support of the Mesoamerican Biological Corridor through the Mayan forest is our
best bet for ensuring the survival of these majestic birds.
Acknowledgements
We thank J. González-Astorga and D. Piñero for insightful discussions during the course of this
study. Comments and suggestions by C. Arizmendi, C. Gutiérrez, A. Navarro, O. Rojas-Soto, and
two anonymous reviewers greatly improved this manuscript. We are very thankful to the
following individuals and institutions: Lacandona community, Ejido Reforma Agraria
community, and the Comisión Nacional de Áreas Naturales Protegidas (México), the Wildlife
Conservation Society and Aviarios Mariana (Guatemala), and Parque Montaña Guacamaya
(Honduras). LMGF received a Doctoral Scholarship from the Mexican government (CONACyT
159239). This research was supported by grant from the Mexican government (CONACyT
35202-V).

53
References
Álvarez del Toro, M., 1985. Así Era Chiapas. McArthur Fundation, Instituto de Historia Natural
Chiapas, México.
Ankersen, T.T., Arriola, L.A., 2001. La Encrucijada de la Conservación y el Desarrollo: El Reto
de la Selva Maya. Mayan Forest Coalition, Men and Biosphere Program USA.
http://conservation.law.ufl.edu/pdf/maya_spanish.pdf (last access: September 4, 2008).
Avise, J.C. 2000. Phylogeography: The History and Formation of Species. Harvard University
Press.
Avise, J.C., Walker, D. Johns, G.C., 1998. Speciation durations and Pleistocene effects on
vertebrate phylogeography. Proceedings of the Royal Society of London Biological Sciences
265, 1707-1712.
Behrensmeyer, A.K., Damuth, J.D., DiMichele, W.A., Potts, R., Sues, H.D., Wing, S.L. 1992.
Terrestrial Ecosystems Through Time: Evolutionary Paleoecology of Terrestrial Plants and
Animals. The University of Chicago Press, Chicago.
Binford L.C. 1989. A distributional survey of the birds of the Mexican State of Oaxaca.
Ornithological Monographs 43, 99-100.
Birdlife International. 2000. Threatened Birds of the World. The Official Source for Birds on the
IUCN Red List. Lynx Editions and BirdLife International, Barcelona and Cambridge.
Bjork, R. 2004. Delineating pattern and processes in tropical lowland: Mealy parrot migration
dynamics as a guide for regional conservation plans. PhD Dissertation. Oregon State University.

54
Carreón, A.G, 2000. Ecología y biología de la conservación de la guacamaya roja (Ara macao) en
la Selva Lacandona, Chiapas, México. Tesis de Maestría. Universidad Nacional Autónoma de
México.
CITES, 2001. Convención sobre el comercio internacional de especies amenazadas de fauna y
flora silvestres. Decimoséptima reunión del Comité de Fauna. Hanoi, Viet Nam.
http://www.cites.org/esp/com/AC/17/S17-08-1.pdf (last access: September 4, 2008).
Clement, M., Posada, D., Crandall, K.A., 2000. TCS: A computer program to estimate gene
genealogies. Molecular Ecology 9, 1657-1660.
Conservation International, 2004. Perfil del ecosistema: Región norte del hotspot de
biodiversidad de Mesoamérica. Belize, Guatemala, Mexico.
http://www.cepf.net/xp/cepf/static/pdfs/Final.Spanish.Mesoamerica.NorthernMesoamerica.EP.pd
f (last access: September 4, 2008).
Duverger, C., 1999. Mesoamérica Arte y Antropología. CONACULTA-Landucci, Paris.
Eberhard, J.R., Bermingham, E., 2004. Phylogeny and biogeography of the Amazona
ochrocephala (Aves: Psittacidae) complex. Auk 121, 318-332.
Ewens, W.J., Brockwell, P.J., Gani, J.M., Resnick, S.I., 1987. Minimum viable populations in the
presence of catastrophes, in: Soulé, M.E. (Ed.), Viable Populations for Conservation. Cambridge
University Press, Cambridge, pp. 57-68.
Excoffier, L., Laval, G., Schneider, S., 2005. Arlequin ver. 3.0: An integrated software package
for population genetics data analysis. Evolutionary Bioinformatics Online 1, 47-50.
Forshaw, J.M., 1989. Parrots of the World. 3rd edn. Melbourne.

55
Fuerst, G.S., Austin, C.C., 2004. Population genetic structure of the prairie skink (Eumeces
septentrionalis): Nested clade analysis of post-Pleistocene populations. Journal of Herpetology
38, 257-26.
Glenn, C.J., Avise, J.C., 1998. A comparative summary of genetic distances in vertebrates from
the mitochondrial cytochrome b gene. Molecular Biology and Evolution 15, 1481-1490.
Groth. J.G., Barrowclough, G.F., 1999. Basal divergences in birds and the phylogenetic utility of
the nuclear RAG-1 gene. Molecular Phylogenetics and Evolution 12, 115-123.
Hackett, S.J. 1996. Molecular phylogenetic and biogeography of tanagers in the genus
Ramphocelus (Aves). Molecular Phylogenetics and Evolution 5:368-382.
Harpending, H., 1994. Signature of ancient population growth in allow-resolution mitochondrial
DNA mismatch distribution. Human Biology 66, 591-600.
Hedrick, P.W., 2000. Genetics of populations. 2nd edn. Jones and Bartlett Publishers, Sudbury,
Massachusetts.
Huelsenbeck, J.P., Ronquist, F., 2001. MrBayes: Bayesian inference of phylogeny.
Bioinformatics 17, 754-755.
Huelsenbeck, J.P., Larget, B., Miller, R.E., Ronquist, F., 2002. Potential applications and pitfalls
of Bayesian inference of phylogeny. Systematic Biology 51, 673-688.
InfoNatura: Animals and Ecosystems of Latin America [web application]. 2007. Version 5.0 .
Arlington, Virginia (USA): NatureServe. Available: http://www.natureserve.org/infonatura.
(Accessed: December 10, 2008 ).

56
Iñigo-Elías, E.E., 1996. Ecology and Breeding Biology of the Scarlet Macaw (Ara macao) in the
Usumacinta Drainage Basin of México and Guatemala. Ph.D. Dissertation. University of Florida.
Gainesville, Florida, USA.
Iñigo-Elías, E. E. 1999. Las guacamayas verde y escarlata en México. Biodiversitas 5,7-11.
Juniper, T., Parr, M., 1998. Parrots: A Guide to the Parrots of the World. Pica Press, Sussex.
Kainer, M., 1991. Conservation of the Scarlet Macaw (Ara macao): Subtropical moist forest life
zone, Belize, Central America. In: Proceedings of the First Mesoamerican Workshop on the
Conservation and Management of Macaws. Jack Clinton-Eitniear, ed. Center for the Study of
Tropical Birds, Inc. San Antonio, Texas, USA, pp. 5-10.
Lande, R., 1988. Genetics and demography in biological conservation. Science 241, 1455-1460.
Lovette, I.J., Bermingham, E., Ricklefs, R.E., 1999. Mitochondrial DNA phylogeography and the
conservation of endangered Lesser Antillean Icterus orioles. Conservation Biology 13, 1088-
1096.
Lynch, M., Crease, T.J., 1990. The analysis of population survey data on DNA sequence
variation. Molecular Biology and Evolution 7, 377-394.
Macías-Caballero, C., E. E. Iñigo-Elías and E. C. Enkerlin-Hoeflich, 2000. Proyecto para la
Conservación, Manejo y Aprovechamiento Sustentable de los Psitácidos en México. Secretaria
de Medio Ambiente, Recursos Naturales y Pesca (Semarnap). D.F., México, 145 pp.
Martínez-Sánchez, J. C., 1991. Distributional and conservation of macaws in Nicaragua. In:
Proceedings of the First Mesoamerican Workshop on the Conservation and Management of
Macaws. Jack Clinton-Eitniear, ed. Center for the Study of Tropical Birds, Inc. San Antonio,
Texas, USA pp 19-22.

57
Nei, M., Li., W.H., 1979. Mathematical model for studying genetic variation in terms of
restriction endonucleases. Proceedings of National Academic of Science 76, 5269-5273.
Nei, M., Kumar, S., 2000. Molecular Evolution and Phylogenetics. Oxford University Press, New
York.
Newton, A.C., Allnutt, T.R., Gilles, A.C.M., Lowe, A.J., Ennos, R.A., 1999. Molecular
phylogeography, intraspecific variation and conservation of tree species. TREE 14, 140-145.
O'Brien, S.J., Roelke, M.E., Marker, L., Newman, A., Winkler, C.A., Meltzer, D., Colly, L.,
Evermann, J.F., Bush, M., Wildt, D. E., 1985. Genetic basis for species vulnerability in the
cheetah. Science 227, 1428-1434. doi: 10.1126/science.2983425
Palerm, A., 1972. Agricultura y Civilización en Mesoamérica. Secretaría de Educación Pública,
México.
Partners in Flight, 2001. La Guacamaya Roja bajo gran peligro de extinción. La Tangara 33.
http://www.partnersinflight.org/latangara/febmar01s.htm (last access: September 4, 2008).
Pérez-Pérez, E. S. 1998. Evaluación del hábitat disponible para la guacamaya roja (Ara macao)
en Petén, Guatemala. Bs. Thesis. Facultad de Ciencias Químicas y Farmacia. Universidad de San
Carlos de Guatemala. Guatemala.
Posada, D., Crandall, K.A., 1998. Modeltest: Testing the model of DNA substitution.
Bioinformatics 14, 817-818.
Ramos-Onsins, S.E., Rozas, J., 2002. Statistical properties of new neutrality tests against
population growth. Molecular Biology and Evolution 19, 2092-2100.
Renton, K., 2000. Scarlet Macaw, in: Reading, R.P., Miller, B. (Eds.), Endangered Animals: A
Reference Guide to Conflicting Issues. Greenwood Press, Westport, Connecticut, pp. 253-257.

58
Rogers, A.R., Harpending, H., 1992. Population growth makes waves in the distribution of
pairwise genetic differences., Molecular Biology and Evolution 9, 552-569.
Ronquist, F., Huelsenbeck, J.P., 2003. MrBayes 3: Bayesian phylogenetic inference under mixed
models. Bioinformatics Applications Note 19, 1572-1574.
Rozas J., Sánchez-DelBarrio J.C., Messenger X., Rozas R. 2003. DnaSP: DNA polymorphism
analyses by the coalescent and other methods. Bioinformatics 19, 2496-2497.
Sánchez, O., Pineda, M. A., Benítez, H., González, B., Berlanga, H., 1998. Guía de Identificación
para las Aves y Mamíferos Silvestres de Mayor Comercio en México Protegidos por la CITES.
Secretaría de Medio Ambiente, Recursos Naturales y Pesca, Comisión Nacional para el
Conocimiento y Uso de la Biodiversidad, México.
Sheppard, C., 1995. Captive propagation and avian conservation, in: Gibbons Jr. E., Durrant, B.,
Demarest, J. (Eds.), Conservation of Endangered Species in Captivity. State University of New
York Press, Albany, pp. 227-240.
Shonewald-Cox, C.M., Chambers, S.M., MacBryde, B., Thomas, W.L., 1983. Genetics and
Conservation: A Reference for Managing Wild Animals and Plants Populations. Benjamin
Cummings. Melo Park, California.
Sibley, C.G., Monroe, B.L., 1990. Distribution and Classification of the Birds of the World. Yale
University Press, New Haven, Connecticut.
Singer-Sam, J., Tanguay, R.L., Riggs, A.D., 1989. Use of Chelex to improbe PCR signals from a
small number of cells. Amplifications (A forum for PCR users) 3, 11.
Slatkin, M., 1991. Inbreeding coefficients and coalescence times. Genetical Research 58, 167-
175.

59
Snyder, N., McGowan, P., Gilardi, J., Grajal, A., 2000. Parrots. Status Survey and Conservation
Action Plan 2000–2004. IUCN, Gland, Switzerland and Cambridge.
Soulé, M.E., 1987. Viable Populations for Conservation. Cambridge University Press,
Cambridge.
Street, F.A., 1981. Tropical paleoenvironments. Progress in Physical Geography 5, 157-185.
Tavares, E.S., Baker, A.J., Pereira, S.L., Miyaki, C.Y., 2006. Phylogenetic relationships and
historical biogeography of Neotropical parrots (Psittaciformes: Psittacidae: Arini) inferred from
mitochondrial and nuclear DNA sequences. Systematic Biology 55, 454-470.
Templeton, A.R., 1998. Nested clade analyses of phylogeographic data: Testing hypotheses about
gene flow and population history. Molecular Ecology 7, 381-397.
Templeton, A.R., 2001. Using phylogeographic analyses of gene trees to test species status and
processes. Molecular Ecology 10, 779-791.
Templeton, A.R., Routman, E., Phillips, C.A., 1995. Separating population structure from
population history: A cladistic analysis of the geographical distribution of mitochondrial DNA
haplotypes in the Tiger salamader, Ambystoma tigrinum. Genetics 140, 767-782.
Thorn, S., 1991. The current situation of macaws in Honduras. In: Proceedings of the First
Mesoamerican Workshop on the Conservation and Management of Macaws. Jack Clinton-
Eitniear, ed. Center for the Study of Tropical Birds, Inc. San Antonio, Texas, USA, pp. 17.
Thurber, W.A., Serrano, J.F., Sermeño, A., Benítez, M., 1987. Status of uncommon and
previously unreported birds of El Salvador. Proceedings of the Western Foundation of Vertebrate
Zoology 3, 109-293.

60
Vaughan, C., Nemeth, N., Marineros, L., 2006. Scarlet Macaw, Ara macao, (Psittaciformes:
Psittacidae) diet in central Pacific Costa Rica. Revista de Biologia Tropical 54, 919-926.
Wiedenfeld, D.A., 1994. A new subspecies of Scarlet Macaw and its status and conservation.
Ornitología Neotropical 5, 99-104.
Wright, S., 1921. Systems of mating. Genetics 6, 111-178.
Wrigth, S., 1969. Evolution and the Genetics of Populations. The Theory of Gene Frequencies.
University of Chicago Press, Chicago.
Wright T.F., Wilkinson, G.S., 2001. Population genetic structure and vocal dialects in an amazon
parrot. Proceeding of Royal Society of London Serie B 268, 609-616.
Yuhki, N., O’Brian, S. J., 1990. DNA variation of the mammalian major histocompatibility
complex reflects genomic diversity and population history. Proceedings of the National Academy
of Sciences USA 87, 836-840.

61
Table II.1 - Haplotype list and distribution
ND2 ND5 RAG-1 Collection site
0046
0068
0097
0107
0151
0205
0262
0293
0316
0341
0355
0394
0408
0458
0555
0576
0613
0658
096
0745
0877
1036
1092
1103
1146
1211
1230
1261
1363
1479
1545
Bel
z
Chi
I
Chi
II
Gua
I
Gua
II
Hond
n
Hap01 A T C A T C G T A C C A T C T A C C T C A T G A C C G T A C T 0 0 0 0 1 0 1
Hap02 . . . . . . . . . . . . . . . . . . . . . . . G T . A . . . . 0 0 0 0 1 0 1
Hap03 . . . . . . . . . . . . . . . . . . . . . C . . T . A . . . . 0 0 0 0 1 0 1
Hap04 . . . . C . . . . . . . . . . . . . . . . . . . T . A . . . . 0 0 0 0 1 0 1
Hap05 . . . . . . . . . . . G . . . . . . . . . . . . T . A . . . . 0 0 0 0 1 0 1
Hap06 . . . . . . . . . . . . . . . . . . . . . . . . T . A . . . . 0 3 0 2 2 0 7
Hap07 . . . . . T . . . . . . . . . . . . . . . . A . T . A . . . . 0 0 0 0 1 0 1
Hap08 . . . . . T . . . . . . . . . . . . C . . . . . T . A . . . . 1 0 0 0 0 0 1
Hap09 . . . . . T . . . . . . . . . . . . . . . . . . T . A . . . . 1 2 3 11 0 6 23
Hap10 . . . . . . . . . . . . . T . . . . . . . . . . T . A . . . . 0 0 1 0 0 0 1
Hap11 . . . . . . . . . . . . . . . . . . . . . . . . T . A . C . . 0 0 1 0 0 0 1
Hap12 . . . . . T A . G . . . C . C . . . C . . . . . T . A . . . . 0 0 0 1 0 0 1
Hap13 . . . . . T . . . . . . . . . . . . . . . . . . T . A . C . . 0 0 0 0 0 1 1
Hap14 . . . . . T . . . . T . . . . . . . . . . . . . T . A . . . . 0 0 0 0 0 1 1
Hap15 . . . . . . . . . . . . . . . G . . . . . . . . T . A . . . . 0 0 0 0 0 1 1
Hap16 . . . . . . . . . . . . . . . . . . . . G . . . T . A . . . . 0 0 0 0 0 1 1
Hap17 . . . . . T . G . . . . . . . . . . . . . . . . T . A . . T . 0 0 0 0 0 1 1
Hap18 . C . . . T . . . . . . C . . . . T . . . . . . T . A . . . . 0 0 0 0 0 1 1
Hap19 . . . . . T . . . . . . . . . . . . . . . . . . T T A . . . . 0 0 0 0 0 2 2
Hap20 . . . . . T . . . . . . . . . . A . . . . . . . T . A . . . . 0 0 0 0 0 1 1
Hap21 . C . . . T . . . . . . . . . . . T . . . . . . T . A . . . . 0 0 0 0 0 1 1
Hap22 . . . . . T . . . T . . . . . . . . . . . . . . T . A . . . . 0 0 0 1 0 0 1
Hap23 . . . . . . . . . . . . . . . . . . . T . . . . T . A . C . . 0 1 0 0 0 0 1
Hap24 G . G T . T . . . . . . . . . . . . . . . . . . T . A . . . . 0 1 0 0 0 0 1
Hap25 . . . . . . . . . . . . . . . . . . . . . . . . T . A . . . C 0 1 0 0 0 0 1
Hap26 . . . . . T . . . . . . . . . . . . . . . . . . T . A C . . . 0 1 0 0 0 0 1
Belz: Belize, ChiI: Chiapas I, ChiII: Chiapas II, GuaI: Guatemala I, GuaII: Guatemala II, Hond: Honduras, n: absolute haplotype frequency.

62
Table II.2 - Genetic diversity and demographic parameters within the Scarlet Macaw populations
Population n S π sd π H h sd h R2 R τ θ Ne
Belize 2 2 0.0013 0.0016 2 1.0000 0.5000 0.5000 2.0000 2.0000 0.0013 33.4525
Chiapas I 9 8 0.0014 0.0009 6 0.8889 0.0910 0.1334a 0.0617 1.7870 0.0019 49.2336
Chiapas II 5 3 0.0009 0.0008 3 0.7000 0.2184 0.1915a 1.0700 1.4000 0.0009 24.0858
Guatemala I 15 7 0.0007 0.0005 4 0.4670 0.1480 0.1801 0.1531 0.5770 0.0014 36.0084
Guatemala II 8 8 0.0013 0.0009 7 0.9643 0.0772 0.0884b 0.1365 2.0000 0.0020 51.6071
Honduras 16 12 0.0012 0.0008 10 0.8667 0.0793 0.0642b 0.0425 1.9330 0.0023 60.4886
Overall 55 31 0.0012 0.0002 26 0.8148 0.0510 0.0281b 0.0352 1.2470 0.0043 113.3256
n: sample size, S: segregated sites, : nucleotide diversity, sd : ’s standard deviation, H: number of haplotypes, h:
haplotype diversity, sd h: h’s standard deviation, R2: Ramos-Onsins and Rozas statistic (a P < 0.05,
b P > 0.01), r:
raggedness, τ: (Tau) is the date of the growth or decline measured in units of mutational time, Ne: effective population
size.

63
Table II.3 – Fixation index and genetic structure by Analysis of Molecular Variance of Scarlet
macaw populations.
Source of variation d. f. Sum of squares Variance Percentage
Among populations 5 7.940 0.0870 9.40
Within populations 49 41.078 0.8383 90.60
Total 54 49.018 0.9253
Fixation Index FST = 0.0940a
a Significance level: P < 0.01
Table II.4 - Population pairwise values. Absolute number of migrants per generation (M) above
the diagonal, and fixation index (Fst) below the diagonal
Belize Chi I Chi II Gua I Gua II Hond
Belize * 7.3558 95.0000 3.4091 1.3333 ∞
Chi I 0.0636 * ∞ 4.3767 18.8120 6.1261
Chi II 0.0052 -0.0841 * 20.3571 7.1015 ∞
Gua I 0.1279 0.1025a 0.0243 * 1.2292 ∞
Gua II 0.2727a 0.0256 0.0658 0.2892
b * 1.7
Hond -0.0071 0.0755a -0.0169 -0.0005 0.2248 *
Significance level: a P < 0.05,
b P < 0.01,
c P < 0.001; ∞ = infinite.

64
Fig. II.1. Mesoamerican Scarlet macaw collection sites. Numbers indicate the collecting sites:
Chiapas I (1), Chiapas II (2), Guatemala I (3), Guatemala II (4), Belize (5), and Honduras (6).
The inset shows the historical distribution of Ara macao (InfoNatura 2007); the polygons (1-6)
are the putative distribution of the A. m. cyanoptera remnants populations (CITES 2001). Forest-
covertures’ map was produced by the Conservation Mapping Program of the Center for Applied
Biodiversity Science (Conservation International, June 2005).
Gulf of Mexico
Pacific Ocean
Caribbean Sea
21
34
5
6
100 0 100 200 300 400
Kilometers

65
Fig. II.2. Haplotype genealogy recovered after the Bayesian analysis. Numbers above the nodes
are posterior clade credibility. The haplotype distribution is indicated between parenthesis [Belize
(B), Chiapas I (CI), Chiapas II (CII). Guatemala I (GI), Guatemala II (GII), and Honduras (H)].

66
Fig. II.3. Minimum-length network for the 26 haplotypes of the Mesoamerican Scarlet Macaw.
The area of the box representing each haplotype is proportional to its frequency. Dots correspond
to putative uncollected haplotypes.

67
Fig. II.4. Mismatch distribution plots. Solid line is the expected mismatch distribution under a
population growth-decline model; whereas the dashed line is the empirical mismatch distribution.

68

69
CAPITULO III
DISCUSIÓN GENERAL
Los análisis del polimorfismo del ADN mitocondrial (ADNmt) han sido el método más común
para revelar interrelaciones históricas entre especies y entre poblaciones de la misma especie
(Avise 1986, Harrison 1989; Hudson et al. 1992; Lynch y Crease 1999). La molécula entera de
ADNmt puede ser considerada una unidad genética con múltiples alelos, los cuales pueden ser
usados para trazar genealogías del linaje materno (Taberlet 1996). Sin embargo, los análisis de la
variación genética mediante un solo fragmento de ADNmt únicamente dan a conocer una parte
de esta variación, así que se ha recomendado usar el mayor número de pares de bases para
obtener mejor confiabilidad y abarcar la mayor variabilidad del genoma (Avise 2000).
No obstante, existen algunas dificultades en la interpretación de datos filogeográficos, por
lo tanto, se ha sugerido el uso de marcadores alternativos (p.e., marcadores nucleares; Ballard y
Whitlock 2004). La adición de secuencias de ADN nuclear (ADNn) ha servido para determinar el
nivel de divergencia del ADNmt y conocer la historia evolutiva no materna debido a las
diferencias en las tasas evolutivas, retención de polimorfismo ancestral y en el sorteo de linajes
(Allen y Omland 2003). Algunos genes nucleares evolucionan más rápido que otros y más
lentamente que los mitocondriales. Por lo tanto, el ADNn es un complemento para el análisis
mitocondrial permitiendo rescatar de manera más completa la historia evolutiva y el
polimorfismo ancestral (Sanders y Omland 2003).
El número de haplotipos encontrados está relacionado con el tamaño de muestra, el
tamaño del fragmento de ADN y el número de fragmentos analizados. Para la guacamaya roja
recupere 26 haplotipos, lo cual es mayor al número de haplotipos encontrados en otros psitácidos
(p.e., 19 haplotipos en Amazona auropalliata; Wright y Wilkinson 2001). En las poblaciones de
Ara macao cyanoptera existen dos haplotipos comunes, sugiriendo que uno de ellos es el
ancestral (H09). Además, la presencia de haplotipos raros y únicos en las diferentes poblaciones,
indica que la variación genética es mayor a la esperada (Rogers y Harpending 1992). Sumado a la
tendencia de expansión poblacional se puede especular que existió un efecto de “surfing”
(Excoffier y Ray 2008), esto es, cuando existe un evento de expansión a nuevos territorios, y los

70
alelos raros de las poblaciones localizadas en el límite de la expansión, alcanzan altas frecuencias
debido a una fuerte deriva genética (Edmonds et al. 2004; Klopfstein et al. 2006).
Con una tasa del 2% de mutación en loci mitocondriales y el parámetro de tiempo de
expansión poblacional τ, estimé que la expansión demográfica ocurrió en el Pleistoceno entre
52,000 y 36,000 años atrás. En éste periodo existieron varios eventos de glaciación, el más
reciente entre los 90,000 a 10,000 años del presente (Newton 2003). Durante el Pleistoceno
tardío, comenzó un rápido calentamiento entre los 24,000 y los 18,000 años, extendiéndose hasta
el inicio del Holoceno (Newton 2003; Hewitt 2004). Durante los períodos glaciares e
interglaciares, los efectos de compresión y expansión de las zonas tropicales hacían que se
formaran “hábitats refugio” y continuos de hábitat, respectivamente. Así se conectaban las islas
de hábitat con otras similares aumentando el área de hábitat disponible (Bonnefille et al. 1990;
Newton 2003). Los factores biogeográficos del Pleistoceno promovieron diversificación genética
microevolutiva en muchas especies de aves (Avise y Walker 1998).
Algunas especies de aves de las familias neotropicales Trogonidae y Cracidae, estuvieron
distribuidas en el Neártico hasta el Pleistoceno tardío y el Holoceno temprano (Bochenski 1985;
Newton 2003). Los escenarios del Pleistoceno dieron diferentes resultados en la distribución y la
formación de linajes en diferentes especies (Avise y Walker 1998), llevando en algunas a la
expansión de rango de su distribución a partir de los refugios glaciales (Rising y Avise 1993).
Esto mismo pudo haber pasado con otras poblaciones de aves, como los psitácidos, teniendo una
expansión en su distribución y el consecuente crecimiento poblacional, como lo propuesto con
los resultados obtenidos para Ara macao cyanoptera. Se ha observado en otros taxa en
Mesoamérica una fuerte estructuración genética debida a las oscilaciones climáticas del
Pleistoceno y a la repetida colonización desde el sur durante las expansiones de la vegetación
(p.e., Cedrela odorata, Cavers et al. 2003; Ctenosaura quinquecarinata, Hasbún et al. 2005). Por
lo tanto, los procesos naturales a corto plazo pueden determinar que los linajes tienen la
oportunidad de adaptarse a las condiciones de un nuevo ambiente y contribuir a la estructura de
un nuevo bioma (Behrensmeyer et al. 1992; Avise et al. 1998).
Para el caso de la guacamaya roja Mesoamericana, estimé un proceso de migración
desbalanceado entre poblaciones, con un intercambio de migrantes por generación de bajo a
infinito (continuo). Carreón (2000), observó que el área de actividad promedio y la distancia de
dispersión máxima de la especie son mayores en sitios conservados. Aún con el grado de

71
fragmentación de la Selva Maya, la fracción de variación genética observada entre poblaciones
(9%), así como la estructura histórica recobrada en la genealogía, sugieren que la subespecie
Mesoamericana es una unidad reproductiva cohesiva, que presenta una diversidad genética alta.
Aparentemente, existió una población muy grande de guacamaya roja en Mesoamérica, lo cual
ha mantenido en la actualidad esta alta diversidad por un efecto de amortiguación genética. Este
efecto de amortiguación ha sido de gran ventaja para las poblaciones de A. m. cyanoptera, ya que
aún no se ha reflejado mayor afectación en su estructura genética debida a las actividades
antropogénicas (p.e., fragmentación del hábitat). Las presiones sobre el hábitat y sobre la
guacamaya roja en Mesoamérica, iniciaron hace 30,000 años, ya que los primeros pobladores en
la región se dedicaban a la recolección y a la caza (Palerm 1972). Posteriormente, la gran
ocupación Mesoamericana se da por los Olmecas y más tarde por los Mayas. Estos últimos
comenzaron a colonizar en los años 2,500 a. C. en la región del norte de Petén, Guatemala
(Nakbé y El Mirador; Palerm 1972; Duverger 1999). Durante el florecimiento de la cultura Maya,
para los 300 d. C., la Selva Maya estaba densamente poblada, el comercio era de gran
importancia, realizándose transacciones con pieles, vainilla, plumas y ámbar, principalmente. En
el periodo del máximo esplendor de la cultura Maya, hacia los 600 y 900 d. C., comenzó una
explosión demográfica humana que, junto con factores políticos y cambios climáticos, llevaron
más tarde a un desastre ecológico y a la caída y colapso de esta cultura para el año 1,200 d. C
(Palerm 1972; Duverger 1999).
La presión sobre la Selva Maya se agudizó durante el siglo XX. A mediados de este siglo,
aun se observaban grandes bandadas de guacamayas rojas en la confluencia del Río Jataté y el
Arroyo Jordán (Álvarez del Toro 1985). Unos años más tarde, 1957, Álvarez del Toro (1985)
narra que en la zona de la Selva Lacandona, en la confluencia de los ríos Lacantún y Usumacinta,
existía gran variedad y abundancia de fauna y escasa presencia humana, “…era una verdadera
selva virgen no mancillada por la destrucción humana”. Para 1985 describe haber visto grupos
de cuatro o cinco guacamayas rojas y que en la región de Marqués de Comillas ya existía alta
pérdida de hábitat debida a la colonización y por la deforestación para la agricultura y la
ganadería.
La mayor parte de la deforestación en Centroamérica se ha producido desde 1950, debido
principalmente al cambio de uso de suelo. Se estima que la Selva Maya sufre una de las mayores
tasas de deforestación en el mundo, incluso mayor a las de la Amazonia (Banco Mundial 2001;

72
Conservation International 2004, Kricher 2006). En los 80’s, las tasas anuales de deforestación en
Guatemala era de 1.7%, en Belice de 0.2% y en la Selva Lacandona de 1.06%. Entre 1996 y 2000
estas tasas subieron a casi 3%. Se estima que la pérdida de bosques es de 45 hectáreas por hora
debido, principalmente, a la tala, la invasión agrícola-ganadera, y la construcción de
infraestructura carretera (CIGyG 2005; Amor et al. 2007). En 20 años, se han perdido 200,000
hectáreas anuales convirtiéndose en tierras agrícolas. Por ejemplo, la agricultura y las actividades
forestales representan el 60% del uso de la tierra en Guatemala (Conservation International
2004). Además, para la apertura y limpia del terreno, los agricultores queman sus parcelas,
aumentando el riesgo de incendios. Entre 1990 y 1995 más de 500,000 hectáreas de bosque se
perdieron por este factor. En 1998, más de 2.5 millones de hectáreas en Centroamérica fueron
destruidas por la sequía ocasionada por El Niño e incendios descontrolados. En México se
perdieron unas 850,000 hectáreas; en Guatemala 5,100 km2 entre el Parque Nacional Laguna del
Tigre, el Parque Sierra de Lacandón, Machaquilá y las Montañas Mayas (Conservation
International 2004).
Otro problema que repercute en la fragmentación del hábitat es la construcción de
represas y embalses. Existen propuestas de construcción de represas hidroeléctricas en la cuenca
baja del río Usumacinta en la Selva Lacandona (Conservation International 2004), y en el centro
sur de Belice. El Parque Nacional Chiquibul, la Reserva Arqueológica Caracol y la Reserva
Natural Bladen se encuentran en peligro debido a planes de construcción de un embalse en el Río
Chalillo inundando 800 hectáreas de territorio de importancia en la Selva Maya para la crianza de
guacamaya roja (Ankersen y Arriola 2001).
Asimismo, la explotación petrolera es un asunto crítico en la Reserva de Biosfera Maya,
particularmente en Laguna del Tigre en Guatemala y la zona de Marqués de Comillas en Chiapas,
en donde esta actividad es intensa y la inversión en la exploración y explotación ha aumentado en
años recientes (Conservation International 2004).
Por otro lado, la construcción de carreteras ha propiciado la deforestación. Por ejemplo,
en Guatemala, a lo largo de la carretera que va de El Naranjo a la frontera con México, se
observan aproximadamente 2,500 asentamientos humanos. En la carretera de Flores a Melchor de
Mencos, las áreas deforestadas se caracterizan por la ganadería, y la agricultura de milpa a
pequeña escala. Esta misma carretera se continúa hacia Belmopán, capital de Belice, lo que ha
permitido la entrada de agricultura industrial mecanizada y de empresas ganaderas (Ankersen y

73
Arriola 2001; Amor et al. 2007). Actualmente, en México existe una carretera fronteriza que
rodea la Selva Lacandona. Las imágenes de satélite revelan que la presencia humana va en
aumento a lo largo de esta carretera propiciando la rápida destrucción de la selva (Ankersen y
Arriola 2001).
Los intereses de desarrollo turístico amenazan en fragmentar aun más la Selva Maya en la
zona del Petén, construyéndose una carretera que comunique los sitios arqueológicos de Tikal, en
Guatemala, y Calakmul, en México; al igual que la construcción de la carretera Caobas-Arroyo
Negro (México) a Tikal (Guatemala) (Ankersen y Arriola 2001; Amor et al. 2007). Se ha
determinado que la densidad de carreteras tiene un efecto acumulativo y altamente significativo
sobre la deforestación, además que la construcción de nuevas carreteras promueve el aumento en
el crecimiento poblacional (Amor et al. 2007). El crecimiento poblacional en Mesoamérica es
del 4.5% al año y en algunas zonas hasta del doble, lo cual conduce a procesos de degradación de
bosques, erosión del suelo, contaminación del agua y extinción de especies silvestres (Banco
Mundial 2001).
Extinciones locales de la guacamaya roja mesoamericana pueden darse si los procesos de
fragmentación continúan avanzando rápidamente. Las poblaciones quedarán aisladas y serán
vulnerables por procesos genéticos, demográficos y estocásticos (Soulé 1987; Lande 1988;
Komdeur et al. 1998). Si las áreas protegidas o aquellas donde aun existe un número de viable de
individuos, se ven como fragmentos en un paisaje con una matriz mayor, se viene a la mente la
idea de una metapoblación. Sin embargo, si cada fragmento es una población, no siempre reúne
los requisitos para mantener dicha población a largo plazo (Vandermeer et al. 2007). La
fragmentación limita la dispersión los eventos de dispersión a larga distancia propiciando las
extinciones locales y la reducción de la biodiversidad regional (Hubbell 2001; Vandermeer et al.
2007). Quan (2007) mostró que en especies, como los primates (Alouatta palliata) en donde la
capacidad de dispersión reducida la fragmentación reduce en el tamaño poblacional, así como la
diversidad y flujo genéticos. La posibilidad de dispersión debe ser considerada como un
mecanismo fundamental para evitar la endogamia en poblaciones de vertebrados silvestres
(Szulkin y Sheldon 2008).
De forma preliminar se evaluaron los efectos de la fragmentación sobre la estructura
genética en la guacamaya roja mesoamericana de dos formas. Primero, una prueba de Mantel
mostró que no existe una relación de la distancia entre los fragmentos con el índice de fijación

74
(FST , r = -0.1679, p = 0.63), ni con el flujo génico (Nm, r = 0.4192, p = 0.839). Segundo, una
prueba de correlación mostró que no existen efectos significativos entre el tamaño del fragmento
y los distintos parámetros genéticos estimados en el presente estudio (Cuadro III.1). No cabe
duda de que esto es un efecto de que el proceso severo de fragmentación de la selva Maya es un
fenómeno reciente. Sin embargo, se deben tomar medidas de conservación inmediatas ya que en
tan solo siete años el tamaño poblacional de esta ave, se ha reducido de un estimado de 4000
(Wiedenfeld 1994) a 1000 individuos (CITES 2001). De igual forma, el tamaño efectivo de la
población estimado es de tan solo 113 individuos. Lo cual implica una alarmante susceptibilidad
de disminución de la variabilidad genética por la pérdida de haplotipos raros (Triggs et al. 1989;
Lynch y Lande 1998). Franklin y Frankham (1998) concluyeron que el número efectivo
poblacional crítico recomendado para planes de conservación va de 500 a 1000 individuos.
Cuadro III.1. Superficie estimada de sitios de presencia de Ara macao cyanoptera y correlación
entre el tamaño del área de distribución (log) y descriptores de variabilidad genética en las
poblaciones de Ara macao cyanoptera.
Sitio Superficie (Has) Parámetros r r2 EE P
Belice 201836.96 π 0.2526 0.0638 0.0003 0.6292
Chiapas I 497458.73 H 0.6168 0.3804 2.3310 0.1921
Chiapas II 41568.00 h 0.0858 0.0074 0.1999 0.8715
Guatemala I 685575.00 R2 -0.4021 0.1617 0.1459 0.4294
Guatemala II 848440.00 r -0.6576 0.4325 0.6056 0.1558
Honduras 633775.99 θ 0.8072 0.6517 0.0003 0.0521
Total 2908654.68 Ne 0.7875 0.6201 8.3872 0.0630
: diversidad nucleotídica, H: número de haplotipos, h: diversidad haplotípica, R2: estadístico de
Ramos-Onsins y Rozas, r: raggedness, θ: diversidad genética, Ne: tamaño efectivo de la población
La fragmentación repercute en distinto grado sobre la dinámica de las poblaciones y las
comunidades naturales. De acuerdo a la teoría de metapoblaciones (Levins 1970, Hanski 1999),
una metapoblación consiste de una serie de poblaciones que viven en fragmentos de hábitat

75
discretos, las cuales se mantienen conectadas mediante el movimiento de individuos entre estos
fragmentos. El número de migrantes calculado para las poblaciones de Ara macao cyanoptera y
la fragmentación reportada en su hábitat, pudieran sugerir que la subespecie Mesoamérica se
comportan como una metapoblación. Hanski y Simberloff (1997) mostraron que en una
metapoblación la declinación de la extinción se da en forma lenta y gradual. Por lo tanto, si se
pudieran controlar los factores que amenazan a la guacamaya roja mesoamericana (p.e., pérdida
del hábitat y el tráfico ilegal), las poblaciones de esta especie se mantendrían genéticamente
saludables por largo plazo y probablemente ocurriría una recuperación demográfica de forma
natural.
Implicaciones de manejo
La fuerte disminución del tamaño poblacional es un factor claro para plantear estrategias
de conservación. Los esfuerzos deben enfocarse principalmente al hábitat remanente, así como la
conexión de las poblaciones mediante corredores biológicos y/o translocaciones de individuos.
Ochoa (2007) ha mostrado que el grado de conectividad puede controlar la extinción de las
poblaciones. Las translocaciones han servido para la recuperación de especies y la conservación
de su variabilidad genética (Triggs et al. 1989). Uno de los métodos propuestos para minimizar la
endogamia y la pérdida de variación es el intercambio de un individuo por generación para
producir panmixia (Varvio et al. 1986; Stephen et al. 2005), prevenir la excesiva diferenciación
(Wright 1951; Stephen et al. 2005) y mantener los mismos alelos en las poblaciones (Allendorf
1983). En el caso de la guacamaya roja, el número de migrantes por generación calculado es
suficiente para mantener esta panmixia. Sin embargo, la fragmentación del hábitat y la presencia
de haplotipos endémicos para las localidades, sugiere la translocación dirigida como un método
que maximice la variabilidad entre algunas poblaciones.
El mantenimiento de corredores de vegetación también ayudaría para proteger a otras
especies localizadas en el mismo hábitat. Es relativamente simple mantener conectividad entre las
áreas naturales protegidas (p. e. RB Laguna del Tigre y PN Sierra del Lacandón en Guatemala
con RB Montes Azules en México). Además, se podrían considerar otras zonas no protegidas
para integrarlas a un plan de conservación y conexión, debido a la importancia como puntos de

76
diversidad biológica y/o en la conformación de corredores para la conectividad de la Selva Maya
y en el reforzamiento de iniciativas de corredores biológicos (Banco Mundial 2001, Bjork 2004).
El hallazgo de haplotipos endémicos y la frecuencia relativa por localidad de los
haplotipos ampliamente dispersos, pueden ser una herramienta para la identificación del origen
geográfico de los individuos decomisados o que se encuentren en cautiverio. Así se podrá
disponer de estos individuos para liberación, reintroducción y/o reproducción en cautiverio. Los
programas de reintroducción y translocación deberían considerar la diversidad genética de las
especies para poder evitar problemas como reducción de variabilidad genética (Mock et al.
2004), deriva genética, endogamia y diferenciación genotípica, así como la estructura
filogeográfica histórica (Stephen et al. 2005). La pérdida del potencial genético en las especies
puede incrementar la susceptibilidad a enfermedades dentro de las poblaciones reintroducidas
(Frankel y Soulé 1981), minimizar el potencial adaptativo (Earnhardt 1999; Lifjeld et al. 2002)
y/o disminuir la adecuación (Wrigth 1977; Araki et al. 2007). Por ejemplo, en los programas de
reproducción de animales cautivos se ha observado que la capacidad reproductiva en las tres
primeras generaciones disminuye hasta en un 40% debido a la depresión endogámica producida
por el repetido uso de individuos nacidos en cautiverio como fundadores de nuevos grupos (Araki
et al. 2007). Esto puede ser riesgoso cuando se pretenden realizar reintroducciones o
reforzamientos a las poblaciones silvestres, por lo tanto, se recomienda elegir individuos que
presenten los mismos haplotipos. Los haplotipos identificados en este trabajo pueden servir como
un punto de referencia para llevar a cabo estas reintroducciones.
Otra aplicación de los marcadores genéticos es en el reconocimiento del origen
poblacional-geográfico de los individuos. Esto es potencialmente útil cuando se decomisan
animales silvestres o se revisan documentos de tráfico legal. De esta forma, se puede inferir la
procedencia de los animales involucrados mediante la determinación de haplotipos endémicos y/o
frecuencias haplotípicas.

77
CONCLUSIÓN GENERAL
Los resultados de este trabajo muestran que la baja estructura genética e histórica que
presentan las poblaciones de la Guacamaya roja mesoamericana no ha sido severamente afectada
por la reciente fragmentación del habitad. Por lo tanto, es posible que la perdida de hábitat actual,
aún no haya generado un efecto irreversible en la variabilidad genética de esta especie.
La principal estrategia sugerida con este trabajo es realizar proyectos de conservación,
rehabilitación y conexión de fragmentos de hábitat. La integración de nuevos sitios al sistema de
aéreas naturales protegidas en Mesoamérica permitirá preservar numerosos parches de hábitat
que faciliten la dispersión entre las poblaciones de guacamaya y sus hábitats. Los fragmentos con
mayor área y relativamente conectados con otros fragmentos ocupados requieren protección
inmediata. Las poblaciones con un grado mayor de aislamiento y susceptibilidad de desaparición
requerirán de acciones más drásticas para su conservación como la reubicación o translocación en
alguno de los fragmentos grandes y con disponibilidad de recursos.
A este respecto la propuesta de mantener un corredor biológico mesoamericano permitiría
el mantenimiento genético y la estabilidad de la dinámica poblacional de Ara macao cyanoptera.
También, es recomendable la aplicación de programas de conservación directamente sobre las
poblaciones de guacamaya roja (p. e. monitoreo poblacional, proporcionar y monitorear
continuamente sitios de nidación). Finalmente, es necesario implementar programas eficaces que
logren controlar el tráfico y el comercio ilegal de esta especie.

78

79
REFERENCIAS
Allen, E.S. y K.E. Omland. 2003. Novel intron phylogeny supports plumage convergence in
orioles (Icterus). The Auk 120:961-969.
Allendorf, F. W. 1983. Isolation, gene flow, and genetic differentiation among populations.
Páginas 51-65 in: C. M. Schonewald-Cox, S. M. Chambers, B. MacBryde, y L. Thomas.
editores. Genetics and conservation: a reference for managing wild animal and plant
populations. Benjamin/Cummings, Menlo Park, California.
Álvarez del Toro, M. 1985. ¡Así era Chiapas! John D. y Catherin T. McArthur Fundation,
Fundamat, Instituto de Historia Natural. México.
Amor, C.D., I. Burgués, L.C. Fleck, C. Manterola y J. Reid. 2007. Análisis ambiental y
económico de proyectos carreteros en la Selva Maya, un estudio a escala regional.
Conservation Strategy Fund, Serie técnica No. 9, Mayo.
Ankersen, T.T. y Arriola, L.A. 2001. La encrucijada de la conservación y el desarrollo: el reto de
la Selva Maya. Informe para la Coalición de la Selva Maya y el Directorio de Ecosistemas
Tropicales del programa de Estados Unidos. El Hombre y la Biosfera. Borrador sujeto a
discusión. Febrero, 2001.
Antunes, A., R. Faria, W.E. Johnson, R. Guyomard y P. Alexandrino. 2006. Life on the edge: the
long-term persistence and contrasting spatial genetic structure of distinct Brown Trout life
histories at their ecological limits. Journal of Heredity 97:193-2005.
Araki, H., B. Cooper y M.S. Blouin. 2007. Genetic effect of captive breeding cause a rapid,
cumulative fitness decline in the wild. Science 318:100-103.
Avise, J.C., D. Walker y G.C. Johns. 1998. Speciation durations and Pleistocene effects on
vertebrate phylogeography. Proceedings of the Royal Society of London Biological
Sciences 265:1707–1712.
Avise, J.C. 2000. Phylogeography: the history and formation of species. Harvard University
Press.
Ballard, J.W.O. y M.C. Whitlock. 2004. The incomplete natural history of mitochondria.
Molecular Ecology 13: 729-744.
Banco Mundial. 2001. Proyecto Corredor Biológico Mesoamericano-México. Informe 21136-
ME.

80
Barnett. J.R, V. Ruiz-Gutiérrez, A. Coulon y I.J. Lovette. 2008. Weak genetic structuring
indicates ongoing genes flow across white-ruffed manakin (Corapipo altera) populations
in a high fragmented Costa Rica landscape. Conservation Genetics 9:1403-1412.
Behrensmeyer, A.K., J.D. Damuth, W.A. DiMichele, R. Potts, H.D. Sues y S.L. Wing. 1992.
Terrestrial ecosystems through time. Evolutionary Paleoecology of terrestrial plants and
animals. The University Chicago Press, Chicago, USA.
Bennett P. M., Owens I. P. F. 1997. Variation in extinction risk among birds: Chance or
evolutionary predisposition? Proceedings of the Royal Society of London Series B
Biological Sciences 264:401-408.
Beissinger, S. R. And E. H. Bucher, 1992. Can parrots be conserved through sustainable
harvesting? Bioscience 42:164-173.
Binford L. C. 1989. A distributional survey of the birds of the Mexican State of Oaxaca.
Ornithological Monographs 43:99-100.
Birdlife International. 2000. Threatened birds of the world. The official source for birds on the
IUCN Red List. Barcelona and Cambridge, UK: Lynx Editions and BirdLife International.
Bjork, R.D. 2004. Delineating patterns and process in tropical lowlands: Mealy parrots
migrations dynamics as a guide for regional conservation planning. PhD Dissertation.
Oregon State University.
Bochenski, Z. 1985. The development of western Palearctic avifaunas from fossil evidence.
Proceedings of International Ornithology Congress 18:338-347.
Bonnefille, R. J.C. Roeland y J. Guiot. 1990. Temperature and rainfall estimates for the past
40,000 years in equatorial Africa. Nature 345:347-349.
Brown, L.M., R.R.Ramey II, B. Tamburini y T.A. Gavin. 2004. Population structure and
mitochondrial DNA variation in sedentary Neotropical birds isolated by forest
fragmentation. Conservation Genetics, 5:743-757.
Cantú, G, J.C., M.E. Sánchez, M. Grosselet y J. Silva. 2007. Tráfico ilegal de pericos en México.
Una evaluación detallada. Defenders of Wildlife. México.
Carpenter D.W., Jung R.E., Sites J.W. Jr. 2001. Conservation genetics of the endangered
Shenandoah salamander (Plethodon shenandoah, Plethodontidae). Animal Conservation
4:111-119.

81
Carreón, A.G. 2000. Ecología y biología de la conservación de la guacamaya roja (Ara macao) en
la selva lacandona, Chiapas, México. Tesis de Maestría. Facultad de Ciencias.
Universidad Nacional Autónoma de México.
Carreón, G. y E. Iñigo-Elías. editores. 1998. Reporte y estrategia del taller trinacional para la
conservación y recuperación de la guacamaya escarlata (Ara macao) en la Selva Maya.
Del 28 al 30 de septiembre de 1998. San Cristóbal de las Casas, Chiapas, México.
Cavers S., C. Navarro y J. Lowe. 2003. Chloroplast DNA phylogeography reveals colonization
history of a Neotropical tree, Cedrela odorata L., in Mesoamerica. Molecular Ecology
12:1451-1460.
CIGyG. 2005. Primera fase del Sistema de evaluación y monitoreo para el Corredor Biológico
Mesoamericano – México (Componente de Geomática). Centro de Investigaciones en
Geografía y Geomática “Ing. Jorge L. Tamayo” Informe Final. México.
CITES. 2001. Guacamaya Roja (Ara macao). Información recopilada del taller trinacional
Belice-Guatemala-México, de la revisión de literatura científica, información
proporcionada por algunos gobiernos y comentarios de expertos. México.
Collar, N. J., M. J. Crosby, A. J. Stattersfield. 1994. Birds to watch 2: the world list of threatened
birds. Life Conservation Series No. 4. Bird Life International, Cambridge, U.K.
Collar, N. J., L. P. Gonzaga, N. Krabbe, A. Madroño Nieto, L. G. Naranjo, T. A. Parker III. and
D. C. Wege. 1992. Threatened birds of the Americas. The ICBP/IUCN Red Data Book.
Third ed., part 2. Smithsonian Institution Press, Washington, D.C.
Collar, N. J. y A. T. Juniper. 1992. Dimensions and causes of the parrot conservation crisis.
Páginas 1-24 in: S. R. Beissinger y N. F. R. Snyder. editores. New World parrots in crisis:
Solutions from conservation biology. Smithsonian Institution Press, Washington, D.C.
Conservation International. 2001a. Comunicado de prensa. Guacamaya roja en grave peligro de
extinción. “Guacamayas sin fronteras última oportunidad para conservarlas” Estación
Chajul, Chiapas, del 9 al 13 de Febrero de 2001.
Conservation International, 2001b. Taller sobre Biodiversidad, Áreas Naturales Protegidas y
Corredores Biológicos. Lacandona Siglo XXI, Estrategia conjunta para la conservación de
la biodiversidad. Tuxtla Gutiérrez, Chiapas. 17 de agosto del 2001.

82
Conservation International. 2004. Perfil de Ecosistema Región Norte del Hotspot de
biodiversidad de Mesoamérica. Belice, Guatemala, México. Versión final, 15 de enero de
2004.
Duverger, C. 1999. Mesoamérica, arte y antropología. CONACULTA-Landucci Editores. Paris.
Earnhardt, J.M. 1999. Reintroduction programmes: genetic trade-offs for populations. Animal
Conservation 2:279-286.
Edmonds, C.A., A.S. Lillie y L.L Cavalli-Sforza. 2004. Mutations arising in the wave front of an
expanding population. Proceeding of Natural Academy of Science 101: 975-979.
Ehrlich P. y Ehrlich A. 1981. Extinctions. Random House, San Francisco, USA.
Excoffier, L. y N. Ray. 2008. Surfing during populations expansions promotes genetic
revolutions and structuration. Trends in Ecology and Evolution 23: 347-351.
Forshaw, J.M. 1989. Parrots of the World. 3rd
. Edition. Melbourne.
Forshaw, J.M. y W. T. Cooper. 1977. Parrots of the World. TFH Publications, Inc.
Frankel, O.H., y M.E. Soulé. 1981. Conservation and evolution. Cambridge University Press,
Cambridge, England.
Franklin, I.R. y R. Frankham. 1998. How large must populations be to retain evolutionary
potential? Animal Conservation 1:69-70.
Freeman, A.R., D.E. Machugh, S. McKeown, C. Walzer, D.J. McConnell y D.G. Bradley. 2001.
Sequence variation in the mitochondrial DNA control region of wild African cheetahs
(Acinonyx jubatus). Heredity 86:355–362.
García del Valle, Y., A. Estrada, E. Espinoza, C. Lorenzo y E. Naranjo. 2003. Genética de
poblaciones de monos aulladores (Alouatta pigra) en hábitat continuo y fragmentado en la
Selva Lacandona, México: un estudio preliminar. Universidad y Ciencia, Número
especial II:55-60.
Grativol, A.D., J.D.Ballou y R.C. Fleischer. 2001. Microsatellite variation withing and among
recently fragmented populations of golden lion tamarin (Loentopithecus rosalia).
Conservation Genetics 2:1-9.
Hamann, R. y T. Ankersen. 1996. The Usumacinta river: Building a Framework for Cooperation
between Mexico and Guatemala. Mesoamerican Environmental Law Program. September
1, 1996. Center for Governmental Responsibility University of Florida College of Law,
230 Bruton-Geer, Gainesville, FL 32611.

83
Hanski, I. 1999. Metapopulations ecology. Oxford University Press, Oxford, NY.
Hanski. I. y D. Simberloff. 1997. The metapopulation approach, its history, conceptual domain,
and application to conservation, Pp. 5-26, en: Hanski, I. y M.E. Gilpin, editors,
Metapopulation biology: ecology, genetics & evolution. Academic Press, London, UK.
Harrison. R.G. 1989. Animal mitochondrial DNA as a genetic marker in population and
evolutionary biology. Trends in Ecology and Evolution 8:399-415.
Hasbún, C.R., A. Gómez, G. Köhler y D.H. Lunt. 2005. Mitochondrial DNA phylogeography of
the Mesoamerican spiny-tailed lizard (Ctenosaura quinquecarinata complex): historical
biogeography, species status and conservation. Molecular Ecology 14:3095-3107.
Hedrick, P. W. 2000. Genetics of populations. Second edition. Jones and Bartlett Publishers.
Sudbury, Massachusetts.
Herrera, C.M. y P. Bazaga. 2008. Adding a third dimension to the edge of a species’ range:
altitude and genetic structuring in mountainous landscapes. Heredity 100:275-285.
Hewitt, G.M. 2004. A climate for colonization. Heredity 92:1-2.
Hilton-Taylor, C. 2000. IUCN Red List of Threatened Species. IUCN: Gland, Switzerland.
Hubbell, S.P. 2001. The unified neutral theory of biodiversity and biogeography. Princeton
University Press, Princeton, NJ.
Hudson, R.R., M. Slatkin y W.P. Maddison. 1992. Estimation of levels of gene flow from DNA
sequences data. Genetics 132:583-589.
InfoNatura: Animals and Ecosystems of Latin America [web application]. 2007. Version 5.0.
Arlington, Virginia (USA): NatureServe. Available:
http://www.natureserve.org/infonatura. (Acceso: Diciembre 10, 2008).
Iñigo-Elias, E. E., 1996. Ecology and breeding biology of the Scarlet Macaw (Ara macao) in the
Usumacinta Drainage Basin of México and Guatemala. Unp. Ph.D. Dissertation.
Univesrity of Florida. Gainesville, Florida, USA. 117 pp.
Iñigo-Elias, E. E. and M. Ramos. 1991. The psittacine trade in México. Páginas 380-392 in: J. G.
Robinson y K. H. Redford. editores. Neotropical wildlife: use and conservation.
University of Chicago Press, Chicago, USA.
Juniper, T. y M. Parr. 1998. Parrots. A guide to the parrots of the World. Pica Press, Sussex.
Kainer, M. 1991. Conservation of the Scarlet Macaw (Ara macao): subtropical moist forest life
zone, Belize, Central America. Páginas 5-10 in: J. Clinton-Eitniear. editor. Proceedings of

84
the First Mesoamerican Workshop on the Conservation and Management of Macaws.
Center for the Study of Tropical Birds, Inc. San Antonio, Texas, USA.
Klopfstein, S., M. Curat y L. Excoffier. 2006. The fate of mutations surfing on the wave of a
range expansion. Molecular Biology and Evolution 23: 482-490.
Komdeur, J., A. Kappe y L. van de Zande. 1998. Influence of population on genetic variation and
demography in Seychelles warbles: a field experiment. Animal Conservation 1:203-212.
Kricher, J. 2006. Un compañero neotropical. Una introducción a los animales, plantas y
ecosistemas del trópico del Nuevo Mundo. American Birding Association, Inc.
Lande, R. 1988. Genetics and demography in biological conservation. Science 241:1455-1460.
Levins, R. 1970. Extinction. Lectures and Notes in Mathematics 2:75-107.
Lifjeld, J.T., G. Bjørnstad, O.F. Steen y M. Nesje. 2002. Reduced genetic variation in Norwegian
Peregrine Falcons Falco peregrinus indicated by minisatellite DNA fingerprinting. Ibis
144: E19–E26
Lynch, M, y T.J. Crease. 1990. The analysis of population survey data on DNA sequence
variation. Molecular Biology and Evolution 7:377-394.
Lynch, M. y R. Lande. 1998. The critical effective size for a genetically secure population.
Animal Conservation 1:70-72.
Malone, C.L., C.R.Knapp, J.F. Taylor y S.K. Davis. 2003. Genetic consequences of Pleistocene
fragmentation: isolation, drift, and loss of diversity in rock iguanas (Cyclura).
Conservation Genetics, 4:1-15.
Manzanero, R. 1991. The Status of the Scarlet Macaw (Ara macao) Belize, Central America.
Página 11 in: J. Clinton-Eitniear editor. Proceedings of the First Mesoamerican Workshop
on the Conservation and Management of Macaws. Center for the Study of Tropical Birds,
Inc. San Antonio, Texas, USA.
Martinez-Sanchez, J. C. 1991. Distributional and conservation of macaws in Nicaragua. Página
19-22 in: J. Clinton-Eitniear. editor. Proceedings of the First Mesoamerican Workshop on
the Conservation and Management of Macaws. Center for the Study of Tropical Birds,
Inc. San Antonio, Texas, USA.
Milton, K., J.D. Lozier, and E.A. Lacey. 2008. Genetic structure of a isolated population of
mantled howler monkey (Alouatta palliata) on Barro Colorado Island, Panama.
Conservation Genetic DOI 10.1007/s10592-008-9584-3

85
Mock, K.E., E.K. Latch y O.E. Rhodes. 2004. Assessing losses of genetic diversity due to
translocation: long-term case histories in Merriam’s turkey (Meleagris gallopavo
merriami). Conservation Genetics 5:631-645.
Nader, W., D. Werner y M. Wink. 1999. Genetic diversity of scarlet macaws Ara macao in
reintroduction studies for threatened populations in Costa Rica. Biological Conservation
87:269-272.
Newton, I. 2003. The speciation and biogeography of birds. Academic Press. London, UK.
Ochoa, G.S. 2007. Una perspectiva de paisaje en el manejo del Corredor Biológico
Mesoamericano, Pp. 31-46, en: Harvey, C.A. y J.C. Sáenz, editores, Evaluación y
conservación de biodiversidad en paisajes fragmentados de Mesoamérica. Instituto
Nacional de Biodiversidad (InBio), Santo Domingo de Heredia, Costa Rica
Palerm, A. 1972. Agricultura y civilización en Mesoamérica. Secretaría de Educación Pública.
México.
Pérez, Pérez, E. S. 1998. Evaluación del hábitat disponible para la guacamaya roja (Ara macao)
en Petén, Guatemala. Tesis para obtener el grado de biólogo. Facultad de Ciencias
Químicas y Farmacia. Universidad de San Carlos de Guatemala. Guatemala, abril 1998.
67 pp.
Quan, R.C.L. 2007. Efecto de la fragmentación del hábitat sobre la variabilidad genética en
tropas de mono aullador (Alouatta palliata) del Área de Conservación Tempisque, Costa
Rica, Pp, 475-509, en: Harvey, C.A. y J.C. Sáenz, editores, Evaluación y conservación de
biodiversidad en paisajes fragmentados de Mesoamérica. Instituto Nacional de
Biodiversidad (InBio), Santo Domingo de Heredia, Costa Rica.
Renton, K., 2000. Scarlet Macaw. Páginas 253-257 in: R. P. Reading y B. Miller. editores.
Endangered animals: a reference guide to conflicting issues. Greenwood Press, Westport,
Connecticut, USA.
Rising, J.D. y J.C. Avise. 1993. An application of general concordance principles to the
taxonomy and evolutionary history of the sharp-tailed sparrow (Ammodramus
caudacutus). Auk 110:844-856.
Rogers, A.R. y H. Harpending. 1992. Population growth makes waves in the distribution of
pairwise genetic differences. Molecular Biology and Evolution 9:552-569.

86
Sánchez, O., M. A. Pineda, H. Benítez, B. González y H. Berlanga. 1998. Guía de identificación
para las aves y mamíferos silvestres de mayor comercio en México protegidos por la
CITES, Secretaría de Medio Ambiente, Recursos Naturales y Pesca / Comisión Nacional
para el Conocimiento y Uso de la Biodiversidad, México.
Sanders A.E. y K.E. Omland. 2003. Novel intron phylogeny supports plumage convergence in
orioles (Icterus). The Auk 120:961–969.
Sheppard. 1995. Captive propagation and avian conservation. Páginas 227-240 in: Gibbons E. Jr.,
Durrant B., Demarest J. editores. Conservation of endangered species in captivity. State
University of New York Press, Albany, USA.
Shonewald-Cox, C. M., S. M. Chambers, B. MacBryde y W. L. Thomas. 1983. Genetics and
conservation: a reference for managing wild animals and plants populations.
Benjamin/Cummings. Melo Park, California, USA.
Snyder, N., McGowan, P., Gilardi, J., and Grajal, A. editores. 2000. Parrots. Status Survey and
Conservation Action Plan 2000–2004. IUCN, Gland, Switzerland and Cambridge, UK.
Solórzano S., A.J. Baker y K. Oyama. 2004. Conservation priorities for resplendent quetzals base
on analysis of mitochondrial DNA control region sequences. The Condor 106: 449-456.
Soulé, M.E. (Ed.) 1987. Viable populations for conservation. Cambridge University Press.
Cambridge. UK.
Stephen, C.L., D.G. Whittaker, D. Gillis, L.L. Cox y O.R. Rhodes Jr. 2005. Genetic
consequences of reintroductions: an example from Oregon pronghorn antelope
(Antilocapra americana). Journal of Wildlife Management 69:1463–1474.
Szulkin, M. y B.C. Sheldon. 2008. Dispersal as a mean of inbreeding avoidance in a wild bird
population. Proceeding of Royal Society of London Serie B, 275:703-711.
Taberlet, P. 1996. The use of mitochondrial DNA control region sequencing in conservation
genetics. Páginas 125-142 in: Smith, T.B. y R.K. Wayne. editores. Molecular genetic
approaches in conservation. Oxford University Press.
Takahashi, C.A. 2006. Necesidad de estudios de variabilidad genética en Ara macao.
Mesoamericana 19:77-81.
Thorn, S. 1991. The current situation of macaws in Honduras. Página 17 in: J. Clinton-Eitniear.
editor. Proceedings of the First Mesoamerican Workshop on the Conservation and

87
Management of Macaws. Center for the Study of Tropical Birds, Inc. San Antonio, Texas,
USA.
Thurber, W.A., J.F. Serrano, A. Sermeño, and M. Benitez. 1987. Status of Uncommon and
previously unreported birds of El Salvador. Western Foundation of Vertebrate Zoology
Los Angeles, California: Vol. 3, No. 3, pp. 203.
Triggs, S.J., R.G. Powlesland y C.H. Dawgherty. 1989. Genetic variation and conservation of
Kakapo (Strigops habroptilus: Psittaciformes). Conservation Biology 3:92-96.
UNEP-WCMC. 2001. Threatened Animals of the World. http://www.unep-wcmc.org
/species/animals/animal_redlist.html. Revisado el 29 Mayo, 2006.
Vandermeer, J.,I, Perfecto, S. Philpott y M.J. Chappell. 2007. Reenfocando la conservación en el
paisaje: la importancia de la matriz, Pp75-104, en: Harvey, C.A. y J.C. Sáenz, editores,
Evaluación y conservación de biodiversidad en paisajes fragmentados de Mesoamérica.
Instituto Nacional de Biodiversidad (InBio), Santo Domingo de Heredia, Costa Rica.
Varvio, S.-L. R. Chakroaborty y M. Nei. 1986. Genetic variation in subdivided populations and
conservation genetics. Heredity 57:189- 198.
Wiedenfeld D.A. 1994. A new subspecies of scarlet macaw and its status and conservation.
Ornitología Neotropical 5:99-104.
Winker. K., G.R. Graves y M.J. Braun. 2000. Genetic differentiations among populations of a
migratory songbird: Limnothlypis swainsonii. Journal of Avian Biology 31:319-328.
Wright, S. 1921. Systems of mating. Genetics 6:111-178.
Wright, S. 1951. The genetical structure of populations. Annals of Eugenics 15:323-354.
Wright, S. 1977. Evolution and the Genetics of Populations. University of Chicago Press.
Chicago, IL. USA.
Wright, S. 1978. Evolution and the genetics of populations. University of Chicago Press,
Chicago, IL. USA.
Wright T.F. y G.S. Wilkinson. 2001. Population genetic structure and vocal dialects in an
amazon parrot. Proceeding of Royal Society of London Serie B 268:609-616.