DNA Presentacion
-
Upload
miguel-rivas -
Category
Documents
-
view
218 -
download
0
Transcript of DNA Presentacion

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 1/103
FUNDAMENTOSDEL DNA
18 Febrero 2016

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 2/103
Nobel 1962

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 3/103
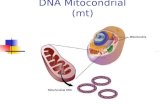
Almacenamiento de información genética
1869 Miescher aisló una sustancia con fósforo de núcleos decélulas, que llamó nucleína
Laboratorio Hoppe-Seyler

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 4/103
Principio de transformación
Streptococcus pneumoniae
Frederick Grifth
La sustancia pasa desdela bacteria muerta a laviva =FACTOR DE
TRANSFORMACIÓN

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 5/103
1944
¿DNA O PROTEÍNA?
Realizaron el experimento conlas bacterias de GrifthStreptococcus pneumoniae

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 6/103
Experimento para la conrmación (1952)
Alfred D. Hershey y Martha Chase
https://www.youtube.com/watch?v=inysl_ydfzQ

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 7/103
Composición del DNA
Erwin Chargaff
Composición del DNA! La composición del DNA generalmente varía de una
especie a otra.! El DNA aislado de diferentes tejidos de la misma
especie tiene la misma composición de bases.! La composición de bases de DNA no cambia en un
organismo con la edad, estado nutricional o cambiode ambiente.
! En todo el DNA, el número de adenosinas, es igual ael número de timinas (A = T) y el número deguanosinas es igual al número de citosinas (C = G)
! A+G = T+C
Humanos A=30.9 T=29.1 G=19.9
C=19.8

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 8/103
DNA
Polímero de deoxironucleótidosSe encuentra en cromosomas, mitocondria y
cloroplastos
BASEAZÚCAR
FOSFATO

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 9/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 10/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 11/103
Los nucleosidos y bases analógas pueden tener usos como
Anticancerígenos
Su ecacia radica en que seune de forma irreversible ala enzima timidilato sintasa ,esencial para la síntesis denucleótidos de timina .
Leucemia linfoblástica aguda (LLA)
Agentes Antirretrovirales
Azidotimina
Aprobado en 1987 como un medicamento indicado para personasinfectadas con el VIH por su efecto retardador de la extensión de lainfección por VIH,

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 12/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 13/103
La secuencia del DNA siempre se sintetiza del 5` a 3´

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 14/103
La estructura secundaria del DNA es unaDOBLE HÉLICE

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 15/103
! 2 cadenas antiparalelas quegiran sobre el mismo eje
! Los grupos fosfato de lascadenas envuelven la periferia
! Bases ocupan el núcleo
f o r m a n d o b a s e scomplementarias A-T, G-C! Se mantiene unida por puentes
de hidrógeno

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 16/103
2 puentes de hidrógeno entre A-T3 Puentes de hidrógeno entre C-G

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 17/103
Apilamiento
Las bases nitrogenadas en el DNA sonplanares y tienen tendencia a apilarse
Fuerzas de apilamiento
Interacciones hidrofóbicas y fuerzas devan der Waals

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 18/103
Formas estructurales del DNA

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 19/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 20/103
Estructura terciaria
El DNA de doble hélice se enrolla alrededor de las histonas
El DNA se une a para formar bras llamadas nucleosomas (10 nm)
Nucleosomas contienen 146 nucleótidos

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 21/103
Nucleosoma
Son unidades globulares repetidas de cromatina que consiste en un complejo histona y D

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 22/103
Compactación del DNA en el cromosoma

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 23/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 24/103
EN RESUMEN
! El DNA esta formado pro 4 bases A, G, T, C, que se encuentran en formaciónlineal por arreglos de enlaces fosfodiéster.
! El DNA está organizado en 2 cadenas antiparalelas por el emparejamiento delas bases A-T y G-C en cadenas complementarias. Estas cadenas forman unadoble hélice alrededor de un eje central.
! Las 3x10 9 pares de bases del DNA humano están organizadas en 23cromosomas

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 25/103
REPLICACIÓN
Proceso de duplicación de la cadena de DNA(Síntesis de una nueva cadena idéntica)
Participantes
Doble hélice del DNA
DNA Polimerasa I y III
Helicasa
Topoisomerasa
SSB Primasas y ligasas

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 26/103
Características generales
1. Complementariedad entre las bases del DNA
Recordemos….

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 27/103
2. Proceso semiconservativo
Cada una de las dos cadenas sirven de molde para la síntesis de nuevas cadenas
3. Dirección de replicación 5´- 3´
4. Primer (cebadores)
Pequeñas unidades de RNA (20 nucleótidos)
5. Primasa
Enzima que introduce el primer
6. DNA polimerasa
Participan en la polimerización del DNA
7. Origen de Replicación

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 28/103
8. Replicación Bidireccional
FRAGMENTOS DE OKASAKI

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 29/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 30/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 31/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 32/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 33/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 34/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 35/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 36/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 37/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 38/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 39/103
DNA pol I DNA pol II DNA pol III
Estructura Monómero109 kD
Monómero90 kD
Multiméro900 kD
Función
Elongación,
corrección yreparación
Elongación,
corrección yreparación
Elongación,
corrección yreparación
AusenciaAfecta la
reparación delDNA
Ninguna conocida Incompatible con lavida

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 40/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 41/103
PCRReacción en cadena de la DNA polimerasa
Técnica desarrollada en 1985 por Kary B. MullisPremio Nobel Química 1993

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 42/103
Técnica de Biología Molecular que tiene por objetivo la amplicación directa de un geno fragmento de DNA
Amplica millones de fragmentos pequeños de DNA hasta 10 Kb en períodos cortos
Amplicación
Detección
PCR

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 43/103
FUNDAMENTOS
Mimetiza el proceso de replicación
Complementaridad
Capacidad del DNA para desnaturalizarse y renaturalizarse
PARTICIPANTES

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 44/103
PARTICIPANTES
1. Molde (Template) DNA
2. Primers
3. DNA PolimerasaMicroorganismos arqueas, son: Thermus aquaticus (polimerasa Taq), Pyrococcus furiosus (Pfu), Thermococcus litoralis (Vent) y Thermus thermophilus (Tth).Generalmente se emplean mezclas del polimerasas muy procesivas (Taq) con otras capaces de hacer corrección de errores (Pfu, Vent).
4. Mg++
5. Deoxynucleótidos dNTP´s
6. Buffer

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 45/103
MOLDE O TEMPLADO
Es la molécula que contiene la región de DNA que quiere amplicar
Se requiere poca cantidad
No se requiere puro
Tiene que se libre de altas concentraciones de EDTA

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 46/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 47/103
Deben ser especícos para la secuencia a amplicar
Deben tener idealmente entre 40-50% CG
Deben evitar estructuras secundarias
Generalmente su longitud debe variar entre 18 y 30 pb

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 48/103
Los primers se ligan a su secuencia complementaria en el DNA target* Un primer compuesto por solo 3 letras, ATT, por ejemplo, tiene una alta probabilidadde encontrar complemento mas de una vez
*A medida que el cebador crece en nucleótidos, la probabilidad de que una secuencia de letras se encuentre repetida se vuelve más remota.
Por ejemplo
Características de un buen Primer

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 49/103
Características de un buen Primer
Temperatura de fusión (Tm) en el intervalo de 50ºC a 65ºC
Temperatura a la cual el 50% de las cadenas seencuentran separadas
Que no formen horquillas > a 3pb
Bajo contenido de GC para evitar exceso de anidad no complementaria

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 50/103
Sólo puede existiruna zona complementaria en el DNA donde el primer se una, lo cuasignica que el primer debe ser irrepetible
La composición de las bases afecta la especicidad de la hibridación así como su temperatLa composciión aleatoria de bases es lo mejor.Evitar primers con secuencias de conformación GCGCGC o ATATAA
Un contenido de G+C alrededor de 40-50% nos proporcionará una buena temperatura dealineamiento
Temperatura de hibridación

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 51/103
Temperatura de hibridación
Se calcula usando la temperatura de fusión (Tm) de los primers
Thibridación = Tm_primer - 4 ºC
Si los primers son complementarios entre si, y se hibridan entre ellos en lugar del DNAmuestra, la eciencia de la PCR se verá afectada drasticamente
La temperatura de hibridación debe ser mutuamente compatible. La máxima diferencia
permisible en la temperatura de los 2 primeros es de 3ºC.
RESUMEN

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 52/103
RESUMEN
ESPECIFICIDAD: Asegurar que a secuencia complementaria sea única
LONGITUD: 17-28 Bases
COMPOSICIÓN DE BASES: El contenido promedio (C+G) en el intervalo de 40-50% yregiones ricas en (A+T) y (G+C)
TM : intervalo de 55-70ºC
Minimizar la posibilidad de formación de estructuras secundarias, horquillas y dímeros

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 53/103
La muestra del DNA, Taq o Pfu, el tampón, los núcleotidostrifosfato y los cebadores son vertido en tubos de paredesdelgados y estos puestos en un termociclador de PCR

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 54/103
CGTTGCGTGCTCGCCTTACCCTCTCAACTCAATTTCTTCAACCCAATTTCTTCGM A F P I P A R Q L F I
CATTTAACCAAGA ATG GCG TTC CCA ATT CCT GCT CGT CAG CTA TTC ATCD G E W R E P I K K N R U P V
GAC GGA GAG TGG AGA GAA CCC ATT AAA AAA AAT CGC ATA CCC GTCI N P S T E E I I G D I P A A
ATC AAT CCG TCC ACT GAA GAA ATC ATC GGT GAT ATT CCG GCA GCCT A E D V E V A V V A A R R A
ACG GCT GAA GAT GTG GAG GTT GCG GTG GTG GCA GCT CGA AGA GCCF R R N N W S A T S G A H R A
TTT AGG AGG AAC AAT TGG TCA GCA ACA TCT GGG GCT CAT CGT GCCT Y L R A I A A K I T E K K D
ACA TAC TTG CGT GCT ATT GCT GCT AAG ATA ACA GAA AAA AAA GATH F V K L E T I D S G K P F D
CAT TTC GTT AAA CTG GAA ACC ATT GAT TCT GGG AAA CCT TTT GATE A V L D I D D V A S C F E Y F
GAA GCA GTG CTG GAC ATT GAT GAC GTT GCT TCA TGT TTT GAA TAT TTTA G Q A E A L D G K Q K A P V
GCC GGA CAA GCA GAA GCT CTT GAT GGT AAA CAA AAG GCT CCA GTCT L P M E R F K S H V L R Q P
ACC CTG CCT ATG GAA AGG TTC AAA AGT CAT GTT CTC AGG CAG CCCL G V V G L I S P W N Y P L L M
CTT GGT GTT GTT GGA TTA ATA TCC CCA TGG AAT TAC CCA CTT CTA ATGA T W K I A P A L A A G C T A
GCT ACA TGG AAA ATT GCT CCA GCA CTT GCT GCT GGG TGT ACA GCTV L K P S E L A S V T C L E F
GTA CTT AAG CCA TCC GAG TTG GCA TCT GTG ACT TGT CTA GAA TTCG E V C N E V G L P P G V L N
GGT GAA GTT TGC AAC GAA GTG GGA CTT CCT CCA GGC GTG TTG AATI L T G L G P D A G A P L V S
ATC TTG ACA GGA TTA GGT CCA GAT GCT GGT GCA CCA TTA GTA TCAH P D V D K I A F T G S S A T
CAC CCC GAT GTT GAC AAG ATT GCC TTT ACT GGG AGT AGT GCC ACTG S K V M A S A A Q L V K P V
GGA AGC AAG GTT ATG GCT TCT GCT GCC CAA TTG GTT AAG CCT GTTT L E L G G K S P I V V F E D
ACA TTA GAA CTT GGG GGT AAA AGT CCT ATT GTA GTG TTT GAA GATV D I D K V V E W T I F G C F W
CTA GAA GTT GGA GCT GTT TGG GTT AAT TGC TCA CAA CCA TGC TTT GTTQ A P W G G I K R S G F G R E
CAA GCT CCT TGG GGA GGC ATC AAG CGT AGT GGT TTT GGA CGT GAAL G E W G I Q N Y L N I K Q V
CTT GGA GAA TGG GGT ATC CAG AAT TAC TTG AAT ATC AAG CAG GTGT Q D I S D E P W G W Y K S P
ACT CAA GAT ATT TCT GAT GAA CCA TGG GGA TGG TAC AAG TCT CCT
TGA
DNA POLIMERASA

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 55/103
DNA POLIMERASA
Taq polimerasaComete un error por cada 10000 nucleótidos
Temperatura 72ºCNo posee actividad correctoraNecesita Mg2+ como cofactor
Mg2+ en altas concentracionesafecta la especicidad,
amplicaciones inespecícas,forma complejos con los dNTP´s

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 56/103
¿CÓMO SE HACE?

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 57/103
Diseño del Primer
Extracción del DNA
PCR
DETECCIÓN
¿CÓMO SE HACE?
ETAPAS

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 58/103
ETAPAS
Desnaturalización Alineamiento
ExtensiónELONGACIÓN FINAL

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 59/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 60/103
¿Cómo podríamos monitorear la PCR?

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 61/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 62/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 63/103
Microscopiade polímero de
agarosa

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 64/103
Uso de “colorantes”

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 65/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 66/103
1 BROMURO DE ETIDIO

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 67/103
1. BROMURO DE ETIDIOEs un agente intercalante

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 68/103
Syber SafeBromuro de Etidio

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 69/103
CGTTGCGTGCTCGCCTTACCCTCTCAACTCAATTTCTTCAACCCAATTTCTTCG

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 70/103
CGTTGCGTGCTCGCCTTACCCTCTCAACTCAATTTCTTCAACCCAATTTCTTCGM A F P I P A R Q L F I
CATTTAACCAAGA ATG GCG TTC CCA ATT CCT GCT CGT CAG CTA TTC ATCD G E W R E P I K K N R U P V
GAC GGA GAG TGG AGA GAA CCC ATT AAA AAA AAT CGC ATA CCC GTCI N P S T E E I I G D I P A A
ATC AAT CCG TCC ACT GAA GAA ATC ATC GGT GAT ATT CCG GCA GCCT A E D V E V A V V A A R R A
ACG GCT GAA GAT GTG GAG GTT GCG GTG GTG GCA GCT CGA AGA GCCF R R N N W S A T S G A H R A
TTT AGG AGG AAC AAT TGG TCA GCA ACA TCT GGG GCT CAT CGT GCCT Y L R A I A A K I T E K K D
ACA TAC TTG CGT GCT ATT GCT GCT AAG ATA ACA GAA AAA AAA GATH F V K L E T I D S G K P F D
CAT TTC GTT AAA CTG GAA ACC ATT GAT TCT GGG AAA CCT TTT GATE A V L D I D D V A S C F E Y F
GAA GCA GTG CTG GAC ATT GAT GAC GTT GCT TCA TGT TTT GAA TAT TTTA G Q A E A L D G K Q K A P V
GCC GGA CAA GCA GAA GCT CTT GAT GGT AAA CAA AAG GCT CCA GTCT L P M E R F K S H V L R Q P
ACC CTG CCT ATG GAA AGG TTC AAA AGT CAT GTT CTC AGG CAG CCCL G V V G L I S P W N Y P L L M
CTT GGT GTT GTT GGA TTA ATA TCC CCA TGG AAT TAC CCA CTT CTA ATGA T W K I A P A L A A G C T A
GCT ACA TGG AAA ATT GCT CCA GCA CTT GCT GCT GGG TGT ACA GCTV L K P S E L A S V T C L E F
GTA CTT AAG CCA TCC GAG TTG GCA TCT GTG ACT TGT CTA GAA TTCG E V C N E V G L P P G V L N
GGT GAA GTT TGC AAC GAA GTG GGA CTT CCT CCA GGC GTG TTG AATI L T G L G P D A G A P L V S
ATC TTG ACA GGA TTA GGT CCA GAT GCT GGT GCA CCA TTA GTA TCAH P D V D K I A F T G S S A T
CAC CCC GAT GTT GAC AAG ATT GCC TTT ACT GGG AGT AGT GCC ACTG S K V M A S A A Q L V K P V
GGA AGC AAG GTT ATG GCT TCT GCT GCC CAA TTG GTT AAG CCT GTTT L E L G G K S P I V V F E D
ACA TTA GAA CTT GGG GGT AAA AGT CCT ATT GTA GTG TTT GAA GATV D I D K V V E W T I F G C F W
CTA GAA GTT GGA GCT GTT TGG GTT AAT TGC TCA CAA CCA TGC TTT GTTQ A P W G G I K R S G F G R E
CAA GCT CCT TGG GGA GGC ATC AAG CGT AGT GGT TTT GGA CGT GAAL G E W G I Q N Y L N I K Q V
CTT GGA GAA TGG GGT ATC CAG AAT TAC TTG AAT ATC AAG CAG GTGT Q D I S D E P W G W Y K S P
ACT CAA GAT ATT TCT GAT GAA CCA TGG GGA TGG TAC AAG TCT CCT
TGA

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 71/103
!"#$%%%$$##$$&$ $%& &#& %%# ##$ $%% ##% &#% #&% #$& #%$ %%# $%#&$# &&$ &$& %&& $&$ &$$ ### $%% $$$ $$$ $$% #&# $%$ ()
(*&%$$$%%&&%%#% %$# #&#$$&&&%%$$ &&$ #&$ &#$ &%# &$% $$&%$&#%& ##% #%# $## %#$ #%% &&& %$$ %%% %%% %%$ &#& %$% !"
+,-./, 01,2$,3
$%& &#& %%# ##$ $%% ##% &#% #&% #$& #%$ %%# $%#&$
!"%&& &&% $%# #$& $$% %$# %%& $$% $%# $$& #$& &%& $#% #$$ &$% $%% %#% &$% &$$ ##$ %&& &&$ %&& %$# $$& %#% ##% ()
()$## ##$ %$& &%# %%$ $%& $$# %%$ %$& %%# &%# #%# %&$ &%% #%$ %$$ $&$ #%$ #%% &&% $## ##% $## $%& %%# $&$ &&$ !)
+,-./, ,/4/,5/
!) $&& $&$ #%% &&$ ##$ %## ##$ %&& ##$ %%# $%# (

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 72/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 73/103
VECTORES DE CLONACIÓN

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 74/103
Los vectores de clonación son moléculas transportadoras que transeren y replican fragmentos de ADN quellevan insertados mediante técnicas de ADN recombinante . Para que sirva de vector, una molécula debe sercapaz de replicarse junto con el fragmento de ADN que transporta. También tiene que tener secuencias de
reconocimiento que permitan la inserción del fragmento de ADN a clonar .
PLÁSMIDOSSon ampliamente usados, proceden de moléculas de DNA de doble cadena extracromosóy se replican autonómamente dentro de la célula
pUC18Es un plásmido muy usado, es derivado del pBR322, 10,000 pb
Bacteriofago20, 000 pb
Cósmidos
Plásmido-lambda 50,000 bp
YACSon cromosomas de levadura 100 kb a 1000kb
Plásmido

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 75/103
Plásmido
1. ORIGEN DE REPLICACIÓNCapaz de hacer copias exactas de si mismo independiente del cromosoma del hosp
2. MARCADORES DE SELECCIÓN
Permite aislar a las células que poseen el gen deseado, generalmente resistencia a uantibiótico
3. SITIO DE CLONACIÓN MULTIPLE (SCM)Sitios de enzimas de restricción en regiones no esenciales. Permite abrir al plásmidinsertar DNA.

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 76/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 77/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 78/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 79/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 80/103
Restricción

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 81/103
Las endonucleasas se denominanenzimas de restricción , debido aque es la forma de defensa de las bacterias contra la invasión povirus, es decir, restringen la invasión por el DNA viral.
Enzimas de restricción

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 82/103
Las enzimas de restricción, también conocidas como endonucleasas, son enzimas que
los enlaces fosfodiester del material genético a partir de una secuencia que reconocen.
Permiten cortar DNA de hebra doble donde reconocen secuencias palindrómicas (secu

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 83/103
Permiten cortar DNA de hebra doble, donde reconocen secuencias palindrómicas (secuque se leen igual en ambas direcciones)
Nomenclatura Ejemplo Corresponde a:E Escherichia Género de la bacteria

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 84/103
E Escherichia Género de la bacteriaco coli Especie de la bacteriaR RY13 Cepa de la bacteriaI La primera enzima identificada Orden de identificación de la enzima
E

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 85/103
Extremos romos
Extremos cohesivos

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 86/103
Extremos cohesivos

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 87/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 88/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 89/103
TRANSFORMACIÓN

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 90/103
CAMBIO HEREDABLE EN UNA CÉLULA U ORGANISMO PRODUCIDO POR LA INTRODUCCIÓN DE UN DNA EX
Puede ser
NATURAL (se han encontrado aproximadamente 40 especiesque pueden realizar este proceso)
ARTIFICIAL (INDUCIDA)

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 91/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 92/103
El “caballito de batalla” es la bacteria Escherichia coli
Es una técnica fundamental en biología molecular: clonación y generarorganismos transgénicos

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 93/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 94/103
Preparar células competentes de
E coli

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 95/103
Preparar células competentes de E. coli
3 mL medioLuria
Incubar toda la
noche a 37 ! C
A= 0.6 – 0.8 a 600 nm
Preparar células competentes de
E.
coli

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 96/103
5000 r.p.m.
5 min4 ! C
3 mL NaCl
Resuspender
5 mL CaCl 2
Resuspender
Preparar células competentes de
Incubar 20 min2500 r.p.m 7
min
!"#$#%&!()*+,+-,+&
LA TRANSFORMACIÓN SE REALIZARÁ POR CHOQUE

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 97/103
1 hr 42 ! C70 s
Inmediatamente enhielo
1 mL medio SOC
Incubar a 37 ! Ccon agitación por 45 min
QTÉRMICO
Al final de la transformación

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 98/103
a de a t a s o ac ó

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 99/103
Células
transformantes
Células
no
transformantes

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 100/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 101/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 102/103

8/19/2019 DNA Presentacion
http://slidepdf.com/reader/full/dna-presentacion 103/103